生物信息学-课堂练习作业生物信息学蛋白质序列分析-课堂练习
生物信息学课后习题

绪论1、生物信息学的概念及其组成部分生物信息学(Bioinformatics):是一门交叉学科,包含了生物信息的获取、处理、储存、分析、解释和应用在内的所有方面,它综合运用了生物学、计算机科学和数学等多方面的知识和方法,来阐述和理解大量生物学数据所包含的生物学意义,并应用于解决生命科学研究和生物技术相关产业中的各种问题。
生物信息学的三个组成部分:①建立可以存放和管理大量生物信息学数据的数据库②研究开发可用于有效分析与挖掘生物学数据的方法、算法和软件工具③使用这些工具去分析和解释不同类型的生物学数据2、生物信息学的主要研究领域①生物数据的建立与搜索②序列比较与相似性搜索③基因组结构注释④蛋白质结构与功能的预测⑤基因组数据分析⑥比较基因组合系统发生遗传学分析⑦功能基因组和蛋白质组学数据分析⑧信号传导、代谢和基因调节途径的构建与描述3、初级数据库二级数据库的概念说出几个数据并说明包含什么数据一级数据库(primary database):数据直接来源于实验获得原始数据,只经过简单的归类、整理和注释。
例如GenBank、EMBL、DDBJ、SWISSPORT、PDB二级数据库(secondary database):在一级数据库、实验数据和理解分析的基础上针对特定的目标衍生而来,是对生物学知识和信息的进一步整理。
例如human genome databases GDB转录因子数据库等4、简述核酸序列的测序①DNA测序一般原理DNA测序一般采用全自动的荧光标记链终止反应完成,该法利用了DNA聚合酶能从脱氧核糖核苷酸(dNTP)延伸但不能从双脱氧核糖核苷酸(ddNTP)延伸的特性,通过加入限量的荧光标记过的双脱氧核苷酸来产生有特定终止碱基的嵌套DNA片段,然后通过聚丙烯酰胺凝胶电泳(PAGE)分离并通过扫描仪读取序列(300-800bp)②基因组测序策略—分而治之---shortgun因为测序反应每次只能测300-800bp故先将基因组分割成一定大小的片段,然后对这些片段分别测序,测完后再将这些片段拼接起来—鸟枪法(shortgun)③一次性测序例如:表达序列标签(EST)是其中的代表,它对随机挑选的cDNA克隆进行两端一次测序得到300-500bp的片段,代表cDNA的一部分。
生物信息学习题

一:名词解释1.生物信息学2.NCBI3.PubMed4.生物芯片5.BLAST6.UniProt7.电子克隆8.EMBL二:填空题1.基因芯片可以分为2. 人类基因组全序列分析分两大步骤即制图和测序,并最终绘制出四张图谱:3. 分子系统发生分析主要分为三个步骤即4. 国际上最主要的三大核酸序列数据库分别是5. 蛋白质得分矩阵有7. 文献是掌握科研进展的最直接方式,目前由NCBI维护的大型文献资源是。
3. 用于核酸序列比对中常见的三种得分矩阵,分别为4. 根据生物芯片探针分子类型的不同,可以将生物芯片哪三种,5. 核酸序列分析所获得的信息主要有(举例说明四个)6. 限制性酶切分析是分子生物学实验中的日常工作之一,这方面最好的限制酶数据库是三:选择题1、如果试图确定一个新蛋白质序列属于哪一个蛋白质家族,或该序列可能包含何种结构域或功能位点,应使用:()A: PROSITE数据库 B: DDBJ数据库C: PIR数据库 D: PDB数据库2、构建序列进化树的一般步骤不包括:()A:建立DNA文库 B:建立数据模型 C:建立取代模型 D:建立进化树3、BLAST教案所程序中,哪个方法是不存在的?()A:BLASTP B:BLASTN C:BLASTX D:BLASTQ4. 以下常见的几个物种,哪一个目前还没有完成全基因组测序:()A: 茶树 B: 玉米 C: 水稻 D: 小鼠5、向核酸序列数据库(GenBank/EMBL/DDBJ)提交数据,应该使用下面哪个软件:()。
A: Blast B:Sequin C:SRS D:Swiss-Model6、在蛋白质序列数据库中比较查询手头未知的蛋白质序列,应使用Blast中哪个具体的算法:()。
A:BLASTX B:tBLASTN C:BLASTP D:BLASTN7、下列中属于一级蛋白质结构数据库的是:()A:EMBL B:DDBJ C:PDB D:SWISS-PROT8、下面不属于SWISS-PROT蛋白质数据库的注释范畴的是:()A: 与其它蛋白质的相似性 B: 蛋白质的二级结构C: 由于缺乏该蛋白质而引起的疾病 D: 核酸的功能描述9、下列属于蛋白质二级结构预测的软件程序是()A: BLASTX B:SOPMA C:DNAstar D:GO10. 如果做DNA结构分析,应该考虑用下面哪个数据库:()A:GenBank B: PIR C:NDB D:UniProt四:简单题1.简述Entrez的设计概念和使用方法?2. 简述生物大分子PDB存储的生物分子种类和数据结构特点?3.简述生物信息学的研究意义?4 简述蛋白质序列分析的基本内容以及常用的软件?5. 简述Swiss-Prot的数据结构?6、简述序列多重比对的意义?7、简述生物信息学的发展历史?五:论述题1.论述蛋白质相互作用研究的意义,传统的实验方法和计算预测方法的应用?2.论述后基因组时代生物信息学面临的挑战和研究策略?3.论述生物信息学的应用?4. 论述如何利用基因芯片数据做聚类分析。
生物信息学课程复习题(南医大)

生物信息学课程习题第一章绪论一、填空1、在年,美国国会批准启动人类基因组计划,拟用年时间测定人类全部条染色体上共个碱基序列的测定。
2、是遗传信息的携带者。
3、蛋白质三维结构测定主要方法有和。
4、理想的抗生素靶标应为微生物细胞所必须,在病原体中高度,且在人体中或与人类基因有。
5、下图例举了一个计算机辅助药物设计的实例,从a图中我们得到了配体上R基团附近的受体上有和残基,具有性,因此可以将R基团设计为性基团,如图b中所示的基团,使得抑制活性比改造前提高了近5000倍。
二、名词HGP(human genome project),EST(expressed sequence tag), SNP(single nucleotide polymorphism),生物信息学(Bioinformatics),药物基因组学(Pharmacogenomics),intron,“Junk DNA”,比较基因组学,蛋白质组学,分子进化树(evolutionary tree),基因组,基因组药物三、简答1、简述生物信息学在药物研究开发领域的应用可体现在哪些方面?2、如何利用基因组信息寻找新的药物作用靶标?3、如何利用人类基因组信息实现个性化治疗,其基于的原理是什么?4、试叙述基因芯片用于疾病诊断的原理,并说明其优缺点。
5、最近甲型流感流行,请设计甲型流感的分子诊断方法,说明其原理。
第二、三章数据库一、单选题1、以下数据库不能用于检索核酸序列的是( B )A. GenBankB. PDBC. EMBLD.DDBJ2、蛋白质结构数据常保存为下面哪一种格式为后缀的文件()A. PDBB. txtC. SeqD. mdb3、下列格式属于FASTA格式的是()A. >seq1B. <seq1C. ATGCCATAD. > ATGCCATAATGCCATA ATGCCATA二、填空题1、阅读以下数据格式,写出以下标注的含义:LOCUS是,DEFINITION是,ACCESSION是,VERSION是,SOURCE是在论文中使用了NCBI数据库中的该序列,应标注该序列的编号,应填。
生物信息学-课堂练习生物信息学蛋白质序列分析-课堂练习

生物信息学蛋白质序列分析-课堂练习ZNF395, 全称为Zinc Finger Protein395, 又被称为PBF,PRF1,DBP2,PRF-1,Si-1-8-14或DKFZp434K1210。
其氨基酸序列为结构域分析:http://www.expasy.ch/prosite/(一)分析蛋白质的一级结构分析蛋白质的pI、Mw、氨基酸组成:Tools and software packages------Identification and characterization-----ProtParamhttp://www.expasy.ch/tools/protparam.html分析蛋白质的疏水性:Primary structure analysis-----ProtScalehttp://www.expasy.ch/tools/protscale.html分析蛋白质的重复序列:Primary structure analysis-----REPhttp://www.embl-heidelberg.de/~andrade/papers/rep/search.html(二)分析蛋白质的二级结构预测蛋白质的?-螺旋和?-折叠结构:Secondary structure prediction-----nnPredict/~nomi/nnpredict.html蛋白质的其它二级结构:Secondary structure prediction-----SOPMA(三)分析蛋白质的三级结构molecular modeling:“tertiary structure prediction ”栏目选择选择一个分析工具,email服务(四)分析膜蛋白质预测膜整合蛋白的跨膜区: Topology prediction------SOSUIhttp://bp.nuap.nagoya-u.ac.jp/sosui/分析膜锚定蛋白的GPI位点:Post-translational modification------big-PI Predictorhttp://mendel.imp.ac.at/sat/gpi/gpi_server.html(五)分析蛋白质的翻译后修饰分析信号肽及其剪切位点: Post-translational modification prediction----SignalIPhttp://www.cbs.dtu.dk/services/SignalP/分析糖链连接点:分析O-连接糖蛋白,Post-translational modification prediction----NetOGlychttp://www.cbs.dtu.dk/services/NetOGlyc/分析N-连接糖蛋白,Post-translational modification prediction----NetNGlyc(六)分析蛋白质的亚细胞定位Topology prediction----PSORT-----WoLF PSORT/(七)分析化学因子作用蛋白质的位点“Identification and characterization ”------“Other prediction or characterization tools”栏目选择“PeptideCutter” 软件http://www.expasy.ch/tools/peptidecutter/1.蛋白基本理化性质分析利用Expasy 软件包中的ProtParam工具(http://www.expasy.ch/tools/protparam.htmL) 进行蛋白的氨基酸组成、分子质量、等电点及疏水性等理化性质的分析。
2-蛋白质序列特征分析-生物信息学

TMPRED在线网页
生命科学学院
用TMPRED分析P51684序列所得到生的命可科能学学院 的7个跨膜螺旋区
生命科学学院
用TMPRED分析P51684序列所得到的7个可 能的跨膜螺旋区的相关性列表
含有卷曲螺旋结构最知名的蛋白质有原癌蛋白 (oncoprotein)c-fos和jun,以及原肌球蛋白 (tropomyosin)。
生命科学学院
利用COILS分析蛋白质的卷曲螺旋
COILS是由Swiss EMBNet维护的预测卷曲螺旋的在 线工具,该软件是基于Lupas算法,将查询序列在一个由 已知包含卷曲螺旋蛋白结构的数据库中进行搜索,同时也 将查询序列与包含球状蛋白序列的PDB次级库进行比较, 并根据两个库搜索得分决定查询序列形成卷曲螺旋的概率。 COILS也可以下载到本地进行运算。
生命科学学院
序列特征分析
Analysis of Sequence Characterristics
一、蛋白质结构 蛋白质的一级结构
生命科学学院
蛋白质的一级结构决定二级结构 蛋白质的二级结构决定三级结构
蛋白质的二级结构
生命科学学院
H表示螺旋 E表示折叠 B表示β桥 G表示3-螺旋 I表示π螺旋 T表示氢键转角 S代表转向
或者全部由碳原子和氢原子组成,因此这类氨基酸不太可 能与水分子形成氢键; 2. 极性氨基酸(polar amino acid),其测链通常由氧原子或 氮原子组成,它们比较容易与水分子形成氢键,因此也称 为亲水氨基酸; 3. 带电氨基酸(charged amino acids),这类氨基酸在生物 pH环境中带有正电或负电。
生命科学学院
生物信息学习题

第六章 分子系统发生分析(问题与练习)
1、构建系统发生树,应使用
A、BLAST
B、FASTA
C、UPGMA
D、Entrez
2、构建系统树的主要方法有
、
、
等。
3、根据生物分子数据进行系统发生分析有哪些优点?
4、在 5 个分类单元所形成的所有可能的有根系统发生树中,随机抽取一棵树是反映真实关
系的树的可能性是多少?从这些分类单元所有可能的无根系统发生树中,随机选择一棵
库
8、TreeBASE 系统主要用于
A、发现新基因 B、系统生物学研究 C、类群间系统发育关系研究 D、序列比对
二、 问答题
1、 为什么说 SWISS-PROT 是最重要的蛋白质一级数据库?
2、 构建蛋白质二级数据库的基本原则是什么?
3、 构建蛋白质二级数据库的主要方法有哪些?
4、 叙述 SCOP 数据库对蛋白质分类的主要依据
第八章 后基因组时代的生物信息学(问题与练习)
1、 比较生物还原论与生物综合论的异同 2、 简述“后基因组生物信息学”的基本研究思路 3、 后基因组生物信息学的主要挑战是什么? 4、 功能基因组系统学的基本特征是什么? 5、 说明后基因组生物信息学对信息流动的最新理解 6、 列举几种预测蛋白质-蛋白质相互作用的理论方法 7、 解释从基因表达水平关联预测蛋白质-蛋白质相互作用的理论方法 8、 解释基因保守近邻法预测蛋白质-蛋白质相互作用的理论方法 9、 解释基因融合法预测蛋白质-蛋白质相互作用的理论方法 10、解释种系轮廓发生法预测蛋白质-蛋白质相互作用的理论方法
1、蛋白质得分矩阵类型有 、
、、
和
等。
2、对位排列主要有局部比对和 三、运算题 1、画出下面两条序列的简单点阵图。将第一条序列放在 x 坐标轴上,将第二条序列放在 y
生物信息学中的蛋白质序列分析与预测研究

生物信息学中的蛋白质序列分析与预测研究蛋白质是生命体中至关重要的分子,它们在细胞功能和结构的调控中发挥着重要的作用。
蛋白质的序列决定了其结构和功能,因此蛋白质序列的分析和预测成为生物信息学研究的重要方向之一。
本文将重点介绍蛋白质序列分析和预测的方法与技术,以及在生物学研究中的应用。
蛋白质序列的分析是指根据蛋白质的氨基酸序列,通过一系列的计算和分析方法,对其结构和功能进行研究的过程。
蛋白质序列分析的方法有很多,其中最常用的包括:比对分析、同源建模、序列特征分析和亚细胞定位预测。
首先,比对分析是蛋白质序列分析的基础方法之一。
通过将待分析的蛋白质序列与已知的蛋白质序列数据库进行比对,可以找到与之相似的序列,进而推测蛋白质的结构和功能。
比对分析常用的工具有BLAST和PSI-BLAST等,它们通过比较序列之间的相似性和一致性,确定序列的保守区域和结构域,从而揭示蛋白质的功能。
其次,同源建模是一种根据已知蛋白质的结构来预测未知蛋白质的结构的方法。
在同源建模中,通过比对已知蛋白质的结构与待预测蛋白质的序列,找到与之相似的蛋白质结构作为模板,并利用模板的结构信息,预测待预测蛋白质的结构。
同源建模的常用工具有SWISS-MODEL和Phyre2等。
同源建模不仅可以预测蛋白质的三维结构,还可以提供结构功能的启示,从而推测其功能。
另外,序列特征分析也是蛋白质序列分析的重要方向之一。
序列特征分析通过对蛋白质序列中的特定模式、保守区域和功能位点进行分析,揭示蛋白质的结构和功能。
常用的序列特征分析方法包括信号肽预测、跨膜区域识别、功能位点预测和蛋白质域识别等。
这些方法通过分析蛋白质序列中的特定特征,揭示蛋白质的功能和结构。
最后,亚细胞定位预测是蛋白质序列分析的一个重要方向。
蛋白质在细胞中的定位决定了其在细胞内发挥的功能,因此准确预测蛋白质的亚细胞定位对于理解其功能至关重要。
亚细胞定位预测通过分析蛋白质序列中的亚细胞定位信号和保守区域,预测蛋白质的亚细胞定位位置。
《生物信息学》练习题

1、在Genbank中查找以下6个植物蛋白序列:protein1:NP_974673.2; protein2: NP_187969.1; protein3: NP_190855.1; protein4: NP_565618.1; protein5: NP_200511.1; protein6: NP_191407.1 (以FASTA格式)。
(1)用EBI上的ClustalW2工具对其进行多序列比对,分析各蛋白序列之间的同源性。
序列比对结果比对结果表明:protein1:NP_974673.2和protein4: NP_565618.1的亲缘关系最近。
(2)利用Phylip软件,选择距离法构建其进化树(要求写出具体的建树步骤)。
1.将蛋白序列保存为FASTA格式,存于txt文档;2.用Clustalx打开txt文本,保存为*.phy文件;3.用seqboot程序打开phy文件,输出结果文件*_seqboot4.用protdist程序打开*_seqboot文件,输出为*_protdist文件5. 用neighbor程序打开*_protdist文件,输出为*_neighbor文件6. 用consense程序打开*_neighbor文件,输出为*_consense文件7.用dratree程序打开*_consense文件得到进化树。
(注:由于seqboot软见无法正常运行,因此进化树无法显示)(3)任意选取其中的一个蛋白进行蛋白质一级序列分析、二级结构预测及三维结构的模拟。
选择protein3: NP_190855.1一级结构网址:/tools/protparam.htmlNumber of amino acids: 456 氨基酸数目Molecular weight: 51154.5 相对分子质量Theoretical pI: 8.69 理论 pI 值Amino acid composition 氨基酸组成Ala (A) 30 6.6%Arg (R) 28 6.1%Asn (N) 15 3.3%Asp (D) 27 5.9%Cys (C) 5 1.1%Gln (Q) 18 3.9%Glu (E) 28 6.1%Gly (G) 37 8.1%His (H) 16 3.5%Ile (I) 16 3.5%Leu (L) 42 9.2%Lys (K) 32 7.0%Met (M) 5 1.1%Phe (F) 17 3.7%Pro (P) 16 3.5%Ser (S) 46 10.1%Thr (T) 21 4.6%Trp (W) 8 1.8%Tyr (Y) 19 4.2%Val (V) 30 6.6%Pyl (O) 0 0.0%Sec (U) 0 0.0%(B) 0 0.0%(Z) 0 0.0%(X) 0 0.0%正/负电荷残基数Total number of negatively charged residues (Asp + Glu): 55Total number of positively charged residues (Arg + Lys): 60Atomic composition: 原子组成Carbon C 2270Hydrogen H 3531Nitrogen N 645Oxygen O 686Sulfur S 10Formula: C2270H3531N645O686S10 分子式Total number of atoms: 7142 总原子数Extinction coefficients: 消光系数Extinction coefficients are in units of M-1 cm-1, at 280 nm measured in water.Ext. coefficient 72560Abs 0.1% (=1 g/l) 1.418, assuming all pairs of Cys residues form cystines Ext. coefficient 72310Abs 0.1% (=1 g/l) 1.414, assuming all Cys residues are reducedEstimated half-life: 半衰期The N-terminal of the sequence considered is M (Met).The estimated half-life is: 30 hours (mammalian reticulocytes, in vitro).>20 hours (yeast, in vivo).>10 hours (Escherichia coli, in vivo).Instability index: 不稳定系数The instability index (II) is computed to be 48.99This classifies the protein as unstable.Aliphatic index: 75.26 脂肪系数Grand average of hydropathicity (GRAVY): -0.554 总平均亲水性/tools/protscale.html蛋白质亲疏水性分析所用氨基酸标度信息Ala: 1.800 Arg: -4.500 Asn: -3.500 Asp: -3.500 Cys: 2.500 Gln: -3.500 Glu: -3.500 Gly: -0.400 His: -3.200 Ile: 4.500 Leu: 3.800 Lys: -3.900 Met: 1.900 Phe: 2.800 Pro: -1.600 Ser: -0.800 Thr: -0.700 Trp: -0.900 Tyr: -1.300 Val: 4.200 : -3.500 : -3.500 : -0.490分析所用参数信息Weights for window positions 1,..,9, using linear weight variation model:1 2 3 4 5 6 7 8 91.00 1.00 1.00 1.00 1.00 1.00 1.00 1.00 1.00edge center edge跨膜结构预测结果(没有跨膜结构)信号肽分析:二级结构预测三级结构预测网站/~phyre2、在拟南芥基因组数据库中(/)查找编号分别为At4G33050, At3G13600,At3G52870或At2G26190基因,针对所查找的基因进行初步的生物信息学分析(每人任选其中一个基因)。
生物信息学试题及答案

广东海洋大学 2013—— 2014 学年第 一 学期《生物信息学 》课程试题答案课程号: 13432210 √ 考试 √ A 卷 √ 闭卷 □ 考查□ B 卷□ 开卷一、 简答题(一) 生物信息学及主要内容?(3)生物信息学是生物和信息技术的结合,这一学科包括了用来管理、分析和操作大量生物数据集的任何计算工具和方法。
(二) 生物信息学主要由哪三个组成部分?(6)1、 建立可以存放和管理大量生物信息学数据集的数据库;2、 开发确定大数据集中各成员关系的算法和统计方法;3、 使用这些工具来分析和解释不同类型的生物数据,包括DNA ,RNA 和蛋白质序列、蛋白质结构、基因表达以及生化途径。
(三) 存储在GenBank 中DNA 序列的类型?(6) 1、基因组DNA 2、cDNA 3、重组DNA(四) 解释下图说明基因组测序的策略?(6)1、霰弹测序法(shot gun sequencing):随机打碎大DNA 分子,通过很多测序反应来覆盖整个分子,完整的序列通过使用计算机搜索重叠区来重新拼接。
2、克隆重叠群(clone contig)的方法中,DNA 片段用推理的方法亚克隆,并且进行系统的测序直到整个序列完成。
(五) 按制备方式分DNA 芯片的主要类型?(6)1、 原位合成芯片:采用显微光蚀刻等技术在特定部位原位合成寡核苷酸而制备的芯片。
探针较短;2、 DNA 微集阵列:将预先制备的DNA 片段以显微打印的方式有序地固化于支持物表面而制成的芯班级:姓名:学号:试题共页加白纸 2张密封线GDOU-B-11-302片。
探针的来源较灵活。
(六) 解释下图说明用芯片如何测定不同组织中基因表达的差异?(8)1、将要检测的基因用芯片点样仪芯片上2、提取待测样品和对照样品的RNA,分别用用Cy3标定一种RNA,而用Cy5标定另一种RNA。
Cy3发红色荧光,Cy5发绿色荧光。
3、用不同的激发光照射,测定两种样品中DNA的表达量。
生物信息学习题

1、基序(motif):通过多序列比对,将同源序列收集在一起,以得到保守区域。
这些保守区域称为基序(motifs)2、可读框(ORF):没有终止密码子(TGA,TAA或TAG)打断的阅读框。
3、剪切变体:从同一DNA,转录得到不同mRNA,并最终翻译成不同的蛋白质称为剪接变体4、表达标签序列(EST):是从cDNA文库中生成的一些很短的序列(300—500bp),它们代表在特定组织或发育阶段表达的基因,有时可代表特定的cDNA.5、系统发生学:通过比较五种的特征,认为特征相似的五种在遗传学上相近,研究五种之见的进化关系二、填空题(共20分,每空1分)l、列举至少2种权威的核酸序列数据库Genbank 、EMBL 等。
2、列举至少3种权威的蛋白质序列数据库PIR 、Swiss-prot 、MIPs 等。
3、核酸序列比对使用的得分矩阵类型有等价矩阵、BLAST 、和转换-颠换矩阵等。
4、蛋白质结构分类数据库主要有SCOP 和CAH 和PDBsum 等。
5、构建系统树的主要方法有UPGMA法、邻近归并法、Fitch-Margoliash法、最小进化法(ME)、最大似然法(ML)、等。
6、列举至少4中NCBI的服务功能Pubmed 、Entrez 、BLAST 和OMIM 等。
1、为什么说Swiss-Prot是重要的蛋白质序列数据库?SwissProt数据库中的所有序列条目都经过有经验的分子生物学家和蛋白质化学家通过计算机工具并查阅有关文献资料仔细核实。
SIB和EBI共有70多人的研究队伍,专门从事蛋白质序列数据的搜集、整理、分析、注释、发布,力图提供高质量的蛋白质序列和注释信息。
SwissProt数据库的每个条目都有详细的注释,包括结构域、功能位点、跨膜区域、二硫键位置、翻译后修饰、突变体等。
该数据库中还包括了与核酸序列数据库EMBL/GenBank/DDBJ、蛋白质结构数据库PDB以及Prosite、PRINTTS等十多个二次数据库的交叉引用代码。
[试题]生物信息学课后题及答案
![[试题]生物信息学课后题及答案](https://img.taocdn.com/s3/m/72ce385068eae009581b6bd97f1922791688be8b.png)
生物信息学课后习题及答案0(由10级生技一、二班课代表整理)0一、绪论01.你认为,什么是生物信息学?0采用信息科学技术,借助数学、生物学的理论、方法,对各种生物信息(包括核酸、蛋白质等)的收集、加工、储存、分析、解释的一门学科。
02.你认为生物信息学有什么用?对你的生活、研究有影响吗?0(1)主要用于:0在基因组分析方面:生物序列相似性比较及其数据库搜索、基因预测、基因组进化和分子进化、蛋白质结构预测等0在医药方面:新药物设计、基因芯片疾病快速诊断、流行病学研究:SARS、人类基因组计划、基因组计划:基因芯片。
0(2)指导研究和实验方案,减少操作性实验的量;验证实验结果;为实验结果提供更多的支持数据等材料。
03.人类基因组计划与生物信息学有什么关系?0人类基因组计划的实施,促进了测序技术的迅猛发展,从而使实验数据和可利用信息急剧增加,信息的管理和分析成为基因组计划的一项重要的工作。
而这些数据信息的管理、分析、解释和使用促使了生物信息学的产生和迅速发展。
04简述人类基因组研究计划的历程。
0通过国际合作,用15年时间(1990-2005)至少投入30亿美元,构建详细的人类基因组遗传图和物理图,确定人类DNA的全部核苷酸序列,定位约10万基因,并对其他生物进行类似研究。
01990,人类基因组计划正式启动。
01996,完成人类基因组计划的遗传作图,启动模式生物基因组计划。
01998完成人类基因组计划的物理作图,开始人类基因组的大规模测序。
Celera公司加入,与公共领域竞争启动水稻基因组计划。
01999,第五届国际公共领域人类基因组测序会议,加快测序速度。
02000,Celera公司宣布完成果蝇基因组测序,国际公共领域宣布完成第一个植物基因组——拟南芥全基因组的测序工作。
02001,人类基因组“中国卷”的绘制工作宣告完成。
02003,中、美、日、德、法、英等6国科学家宣布人类基因组序列图绘制成功,人类基因组计划的.目标全部实现。
生物信息学中的蛋白质序列分析

生物信息学中的蛋白质序列分析随着生物技术的不断发展,人们对于生物体内各种蛋白质的研究愈发深入。
而蛋白质序列分析则是生物信息学中重要的一环,可以用于蛋白质结构预测、功能分析、进化研究等方面。
在这篇文章中,我们将探讨蛋白质序列分析在生物信息学中的应用以及涉及到的技术和算法。
一、蛋白质序列的组成蛋白质由氨基酸组成,而蛋白质序列指的是氨基酸连接的线性序列。
氨基酸是构成蛋白质的基本单元,不同的氨基酸组合构成不同的蛋白质。
目前已知的氨基酸有20种,它们由不同的侧链和碳氮骨架组成,这种多样性导致了蛋白质具有丰富多样的结构和功能。
二、蛋白质序列分析的应用1、预测蛋白质结构蛋白质结构与其功能息息相关,因此对于蛋白质结构的预测一直是研究的热点问题。
蛋白质序列是进行蛋白质结构预测的重要依据之一。
一般来说,蛋白质结构预测可分为二级结构和三级结构预测。
二级结构指的是蛋白质中α-螺旋、β-折叠和无规则卷曲等局部的结构。
目前,常用的二级结构预测方法有Chou-Fasman算法、GOR算法等。
而三级结构预测指的是蛋白质整体的三维结构,其预测难度更大,目前还没有完全解决。
但是,针对蛋白质结构的许多研究都是基于蛋白质序列的分析和预测。
2、鉴定蛋白质功能蛋白质的功能与其序列和结构有关,因此通过分析蛋白质序列也可以预测蛋白质的功能。
一般来说,蛋白质的功能可以分为三类:催化、结构和调节。
催化作用指的是酶类蛋白质对化学反应的促进作用。
结构作用指的是蛋白质形成结构,对于细胞和组织的形态和机能具有重要作用。
调节作用指的是蛋白质对细胞、胚胎、发育和免疫系统等的调节作用。
对于蛋白质功能的鉴定,目前的方法主要有以下几种:1)基于序列的比对方法;2)结构基因学方法;3)基于基因组的方法。
三、蛋白质序列分析的技术和算法1、BLAST算法BLAST(Basic Local Alignment Search Tool)算法是常用的序列比对算法之一,它通过比对两条序列后,计算两个序列之间的相似性得分。
生物信息学作业题

生物信息学作业题生物信息学作业题绪论1.什么是生物信息学?2.生物信息学有哪些主要研究领域?第一章生物信息学的分子生物学基础1.DNA的双螺旋结构要点是什么?2.什么是基因组和蛋白质组?对它们的研究有何意义?第二章生物信息学的计算机基础1.简述网络操作系统的类型。
第三章核酸序列分析1.什么是全局比对?2.什么是局部比对?有哪些优点?第四章分子进化分析1.分子进化分析具有哪些优点?2. 简述分子进化的中性学说。
第五章基因组分析1. 什么是基因组学?其主要研究内容是什么?2.简述基因预测分析的一般步骤。
第六章蛋白质组分析1. 蛋白质组学的概念和主要研究的大致方向是什么?2. 蛋白质组功能预测的程序是怎样的?第七章生物芯片数据分析1. 什么是生物芯片?2. 生物芯片有哪些方面的应用?第八章核酸与蛋白质结构预测1. RNA二级结构典型的预测方法有哪些?2. 基于统计学的预测蛋白质二级结构的方法有哪些?第九章生物信息学平台与工具软件1. 请利用Clustal X软件对下列6条蛋白质序列进行多重比对(比对结果用BioEdit软件打开,用“截图”方式显示比对结果)。
>1mqngkvkwfn sekgfgfiev eggedvfvhf saiqgegfkt leegqevtfe veqgnrgpqatnvnkk>2mqgkvkwfnn ekgfgfieie gaddvfvhfs aiqgegykal eegqevsfdi tegnrgpqaanvvkl>3mqngkvkwfn sekgfgfiev eggedvfvhf saiqgegfkt leegqevtfe veqgnrgpqatnvnkk>4mqgkvkwfnn ekgfgfieie gaddvfvhfs aiqgegykal eegqevsfdi tegnrgpqaanvvkl>5mqngkvkwfn sekgfgfiev eggedvfvhf saiqgegfkt leegqevtfe veqgnrgpqatnvnkk>6mqgkvkwfnn ekgfgfieie gaddvfvhfs aiqgegykal eegqevsfdi tegnrgpqaanvvkl2. 现有一ZmPti1b蛋白质序列,请用DNAMAN软件分析其二级结构,给出分析结果。
生物信息学作业-序列查找与分析

一、序列(1)从NCBI网站中查找人类钙网蛋白的基因序列,登录号为AY047586.1,序列长度为1402 bp,CDS区为54..1307bp。
序列如图3。
图1. NCBI网站中查找人类钙网蛋白序列图2. 人类钙网蛋白序列的相关信息图3 人类钙网蛋白的FASTA格式序列(2)通过blast比对获得相似性前6条的序列:白犀牛钙网蛋白(XM_004442548.1 )、野猪胸腺克隆(AK398467.1)、鼠的钙网蛋白(X53363.1)、小家鼠钙网蛋白( NM_007591.3)、褐家鼠钙网蛋白( NM_022399.2)、现代人互补DNA克隆( BC107102.2),对7条序列的CDS区进行比对分析,并构建系统进化树。
图4 进行BLAST的界面图5 BLAST之后的结果图6 BLAST之后的结果图7 MAGA的运行结果图8 MEGA的运行结果图9 系统进化树二、对人类钙网蛋白的蛋白质进行一级结构的预测从NCBI中搜索人类钙网蛋白的蛋白序列,其登录号为AAL13126.1,序列如图所示:图10 人类钙网蛋白的蛋白序列通过protparam(/tools/protparam.html)对人类钙网蛋白的蛋白质的基本理化性质进行预测,结果显示该蛋白编码氨基酸数目为417,相对分子质量为48141.5 Da,理论pI值4.29。
图11 protparam的首页图12 蛋白质的氨基酸数目.相对分子质量.理论pI值.氨基酸组成图13 蛋白质的正/负电荷残基数.分子式.总原子数图14 蛋白质的消光系数.半衰期.不稳定系数.脂肪系数.总平均亲水性三、对该蛋白质二级结构进行预测(亲疏水性、跨膜区、结构域等)(1)通过protscale (/tools/protscale.html)网站进行亲疏水性预测。
图15 亲疏水性工具protscale首页图16 亲疏水性预测的结果图17 亲疏水性预测的结果(2)通过http://www.cbs.dtu.dk/services/TMHMM-2.0这个网站,对该蛋白质进行跨膜区预测图19 跨膜区工具TMHMM首页图19 跨膜区预测结果(3)通过(http://smart.embl-heidelberg.de/)这个网站,对该蛋白质进行结构域预测图19 结构域工具smart页面图20 结构域预测结果四、通过(/)这个网站,对该蛋白质三级结构进行预测图21 三维工具swiss-modle页面图22 三级结构预测结果个人收获生物信息学通俗的说法就是利用数学和计算机知识来处理生物数据,在这一个学期内的学习中,不仅学习到了有关生物信息学的一些理论知识,而且也使我们接触到了怎样用现代技术来处理得到的数据,每一步做出来的东西都让我们很惊讶也很惊喜,原来生物世界是这么美妙。
蛋白质序列分析和结构预测 生物信息学

蛋白质序列分析和结构预测【实验目的】1、掌握蛋白质序列检索的操作方法;2、熟悉蛋白质基本性质分析;3、熟悉基于序列同源性分析的蛋白质功能预测,了解基于motif、结构位点、结构功能域数据库的蛋白质功能预测;4、了解蛋白质结构预测。
【实验内容】1、使用Entrez信息查询系统检索人瘦素 (leptin)蛋白质序列;2、使用EXPASY中有关工具对上述蛋白质序列进行分子质量、氨基酸组成等基本性质分析;3、对瘦素蛋白质序列进行基于NCBI/Blast软件的蛋白质同源性分析;4、对瘦素蛋白质序列进行motif结构分析、翻译后修饰等的预测【实验方法】1、瘦素蛋白质序列的检索:(1)调用Internet浏览器并在其地址栏输入Entrez网址/Entrez(2)选择protein;(3)在输入栏输入homo sapiens leptin;(4)点击search后显示序列接受号及序列名称;(5)点击序列接受号后显示序列详细信息;(6)将序列转为FASTA格式保存;2、进入EXPASY网站使用有关软件进行蛋白质序列分析和结构预测。
(1)选择Protparam程序对蛋白质序列进行分子质量、氨基酸组成和等电点等基本性质分析;(2)蛋白质的同源性搜索分析,NCBI的BLAST;(3)在Pattern and profile searches中选择interPro Scan 进行结构域或motif搜索以及有关结构域的结构分析(4)在post-translational modification prediction 选择signalP 对蛋白质序列进行信号肽预测分析【作业】提交使用上述软件对瘦素蛋白质序列进行基本性质分析、同源性分析、motif 结构分析以及信号肽折叠位点预测的结果附:【实验方法】1、瘦素蛋白质序列的检索:(1)调用Internet浏览器并在其地址栏输入Entrez网址(/Entrez);(2)选择protein;(3)在输入栏输入homo sapiens leptin;(4)点击go后显示序列接受号及序列名称;(5)点击序列接受号后显示序列详细信息;(6)将序列转为FASTA格式保存;2、进入EXPASY网站http://www.expasy.ch/tools/使用有关软件进行蛋白质序列分析和结构预测。
2蛋白质序列特征分析~生物信息学全解

蛋白质的亲水性或疏水性
氨基酸的亲疏水性是构成蛋白质折叠的主要驱 动力,一般通过亲水性分布图(hydropathy profile)
反映蛋白质的折叠情况。蛋白质折叠时会形成疏水
内核和亲水表面,同时在潜在跨膜区出现高疏水值 区域,据此可以测定跨膜螺旋等二级结构和蛋白质
表面氨基酸分布。
利用PROTSCALE分析蛋白质的亲水性或疏水性
TMPRED在线网页
用TMPRED分析P51684序列所得到的可能的 7个跨膜螺旋区
用TMPRED分析P51684序列所得到的7个可 能的跨膜螺旋区的相关性列表
用TMPRED分析P51684序列所得到的7个可 能的跨膜螺旋区的建议的跨膜拓扑模型
用TMPRED分析P51684序列所得到的7个 可能的跨膜螺旋区的图形显示结果
工具,TMpred基于对TMbase数据库的统计分析来预测蛋白 质跨膜区和跨膜方向。TMbase来源于Swiss-Prot库,并包含了
每个序列的一些附加信息,如:跨膜结构区域的数量、跨
膜结构域的位置及其侧翼序列的情况。TMpred利用这些信息 并与若干加权矩阵结合来进行预测。 其网址为: /software/TMPRED_form.html
4、信号肽—SIGNAL PEPTIDE
信号肽是指新合成多肽链中用于指导蛋白质跨膜转移 的末端(通常为N末端)的氨基酸序列。信号肽中至少含
有一个带正电荷的氨基酸,中部有一个高度疏水区以通过
序列特征分析
Analysis of Sequence Characterristics
一、蛋白质结构
蛋白质的一级结构
蛋白质的一级结构决定二级结构 蛋白质的二级结构决定三级结构
蛋白质的二级结构Leabharlann H表示螺旋E表示折叠
生物信息学中的蛋白质序列分析与预测方法研究

生物信息学中的蛋白质序列分析与预测方法研究生物信息学是一门将计算机科学与生物学相结合的学科,通过使用计算机算法和工具,对生物数据进行分析和解释。
其中,蛋白质序列分析与预测是生物信息学中的一个重要研究方向。
本文将探讨蛋白质序列分析与预测的方法,并介绍一些常用的工具和算法。
蛋白质是生物体内起着重要功能的生物分子,也是生命活动的基本单位。
蛋白质的结构和功能与其氨基酸序列密切相关。
因此,通过分析和预测蛋白质序列,可以揭示蛋白质的结构、功能和相互作用等重要信息。
在蛋白质序列分析中,一个基本的任务是蛋白质序列的同源性比对。
同源性比对可以揭示不同蛋白质序列之间的相似性,从而推断它们的进化关系和功能。
目前,最常用的同源性比对算法是基于Smith-Waterman算法的BLAST。
BLAST通过将查询序列与数据库中已知序列进行比对,计算相似性得分,并找出最相关的序列。
BLAST不仅可以用于同源性搜索,还可以用于序列注释和多序列比对等任务。
此外,蛋白质序列分析还包括预测蛋白质二级结构、域结构和跨膜区域等。
蛋白质二级结构预测是指根据氨基酸序列,预测蛋白质中α-螺旋、β-折叠等二级结构的比例和位置。
常用的二级结构预测方法包括Chou-Fasman算法、GOR算法和PSIPRED算法等。
这些算法基于已知的氨基酸序列和结构的统计关系,通过机器学习和统计模型来预测蛋白质二级结构。
域结构是指蛋白质中具有独立结构和功能的区域。
通过预测蛋白质的域结构,可以推断蛋白质的功能和相互作用。
域结构预测的方法包括K-最近邻算法、隐马尔可夫模型和神经网络等。
这些方法基于已知的域结构数据库和统计模型,通过比对查询序列和数据库序列的相似性,寻找潜在的域结构。
另一个重要的任务是预测蛋白质跨膜区域。
蛋白质跨膜区域是指蛋白质中穿越细胞膜的区域,对细胞的功能和调控起着重要作用。
跨膜区域的预测可以帮助研究人员理解蛋白质的结构和功能。
目前,跨膜区域预测的方法包括隐马尔可夫模型和神经网络等。
生物信息学作业
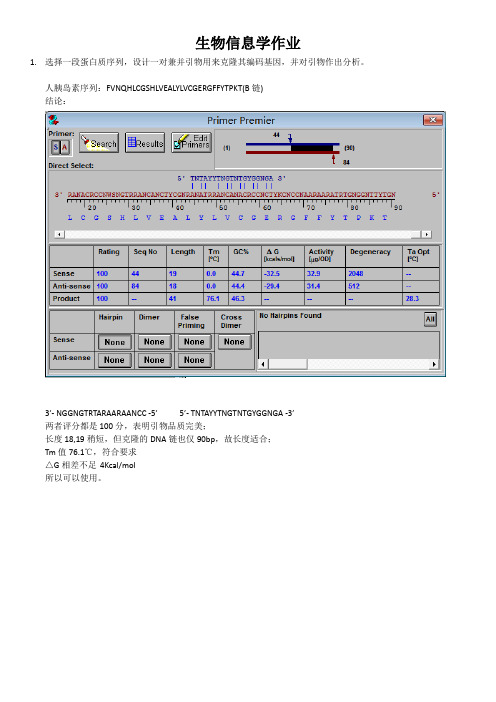
生物信息学作业1.选择一段蛋白质序列,设计一对兼并引物用来克隆其编码基因,并对引物作出分析。
人胰岛素序列:FVNQHLCGSHLVEALYLVCGERGFFYTPKT(B链)结论:3’- NGGNGTRTARAARAANCC -5’ 5’- TNTAYYTNGTNTGYGGNGA -3’两者评分都是100分,表明引物品质完美;长度18,19稍短,但克隆的DNA链也仅90bp,故长度适合;Tm值76.1℃,符合要求△G相差不足4Kcal/mol所以可以使用。
Step1:打开primer premier 5.0 输入蛋白质链,转化为DNA链。
获得DNA链。
2.选择一段基因,预测期编码RNA的二级结构,并分析功能。
取一段基因:ACGCG GGCGG GCATG TGGGC AGCTT TACCC AGTGC TACTG TGCTG GCCAGCACTG AAACA GGGGC ACTGG TTTGG GGTGG ATGAA GGGTA GAAGT GCAAGTTCCA TTGCC TGTGC AATCC CTGCC TTGCT CAGAC CCTGC TCACT CCTCAGGCCC CATCA GCCCC TCAAC TCTGC TAACC ATGGT GGTAG AAATC AGCTACAATA AACCC TGGAG CCAGT AAAAA AAAAA AAAAA AAAAA AAAAA AAAGT点击Fold as RNA点击START点击Draw Stuclture得到RNA二级结构RNA功能预测打开网址http://sidirect2.rnai.jp/输入DNA序列得出结论:。
生物信息学课堂操作练习

生物信息学课堂操作练习一、生物信息学科的发展和研究内容通过下列internet上的自教课程,初步了解不同的数据库和分析工具/2can/Education二、生物数据库1. 熟悉各种数据库。
2. 重点了解GenBank和SWISS-PROT所包含的各种功能和适用范围。
三、关键词或词组为基础的数据库检索1. 熟练掌握Entrez检索体系。
2. 查找与水稻抗病基因Xa21有关的资料(1) 由多少碱基构成?编码多少个氨基酸?(2) exon和intron的位置?(3) 是否有3-D structure数据?1) 由多少碱基构成?编码多少个氨基酸?4623b.p., 1025A.a.;2) exon和intron的位置?Exon: 24~2700,3543~3943 intron: remaining;3) 是否有3-D structure数据?没有.3. 查找C. elegans基因组的资料。
(1) chromosome I的测序是否已完成?(2) 已知的chromosome I的序列有多少碱基?序列发表在哪份杂志上?期号和页码?1) chromosome I的测序是否已完成?完成.2) 已知的chromosome I的序列有多少碱基? 序列发表在哪份杂志上? 期号和页码? 15.0724Mb.p.(15072421b.p.), Science 1999 Jan 1;283(5398):35.4. 查看人类基因组第1染色体上基因的分布。
/mapview/maps.cgi?ORG=hum&MAPS=ideogr,est,loc&LINKS= ON&VERBOSE=ON&CHR=15. 查看Arabidopsis的系谱树,以及Arabidopsis第1染色体上的序列。
比较Arabidopsis基因组的资料提供形式与人类基因组有什么不同(/Taxonomy/Browser/wwwtax.cgi?id=3701,/mapview/maps.cgi?taxid=3702&chr=1)貌似没什么区别……比较Arabidopsis基因组的资料提供形式与人类基因组有什么不同。
- 1、下载文档前请自行甄别文档内容的完整性,平台不提供额外的编辑、内容补充、找答案等附加服务。
- 2、"仅部分预览"的文档,不可在线预览部分如存在完整性等问题,可反馈申请退款(可完整预览的文档不适用该条件!)。
- 3、如文档侵犯您的权益,请联系客服反馈,我们会尽快为您处理(人工客服工作时间:9:00-18:30)。
生物信息学蛋白质序列分析-课堂练习
ZNF395, 全称为Zinc Finger Protein395, 又被称为PBF ,PRF1,DBP2,PRF-1,Si-1-8-14或DKFZp434K1210。
其氨基酸序列为
(一)分析蛋白质的一级结构
ZNF395蛋白的理论等电点为7.17,分子式C 2417H 3775N 679O 741S 23,原子总数为7635,总平均亲水性(GRA VY )为-0.451,脂肪指数64.54,不稳定指数69.57,序列N 末端是M (Met ),估计半衰期是:30小时(哺乳动物网状细胞,离体);>20小时(酵母,体内);>10小时(大肠杆菌,体内)。
在编码的513个氨基酸中,包括48个带负电的氨基酸(天冬氨酸+谷氨酸),33个带正电荷的氨基酸(精氨酸+赖氨酸)。
依据氨基酸分值越低亲水性越强,分值越高疏水性越强的规律,用Expasy 网络服务器的ProtScale Server 在线工具对该氨基酸序列的亲水性/疏水性进行预测,预测结果如图1,分值在-2.800—1.967之间,且绝大部分氨基酸分值为负,故推测该蛋白应为亲水性蛋白。
图1 ZNF395氨基酸序列的亲水性/疏水性分析
(二)分析蛋白质的二级结构
利用SOPMA在线工具对二级结构进行预测,如图2,α螺旋99个占19.30%,延伸链66个占12.87%,β-转角18个占3.51%,无规卷曲330个占64.33%,其二级结构主要由无规卷曲组成。
图2 ZNF395蛋白二级结构预测
注:蓝色表示α螺旋;红色表示延伸链;紫色表示无规则卷曲
(三)分析膜蛋白质
利用在线分析工具TMHMM Server 2.0,对ZNF395氨基酸跨膜结构域进行在线预测和分析,结果表明,该序列编码的蛋白非跨膜蛋白(见图3)。
利用Signal P 3.0 Server在线预测工具对ZNF395蛋白质进行信号肽预测,无信号肽存在(图4)。
图3 ZNF395跨膜结构预测
图4 ZNF395蛋白信号肽预测
利用在线分析工具big-PI Predictor分析ZNF395蛋白的GPI位点,未发现GPI位点。
(四)蛋白质位点分析
利用PredictProtein在线工具(https:/// )对ZNF395蛋白的功能位点进行预测。
ZNF395氨基酸序列含有1个N-糖基化位点,;1个cAMP和cGMP依赖性蛋白激酶磷酸化位点;3个蛋白激酶C磷酸化位点;6个酪蛋白激酶Ⅱ磷酸化位点;1个酪氨酸激酶磷酸化位点;7个N-豆蔻酰化位点;1个酰胺化位点;1个C2H2型锌指域信号(280aa-310aa)。
(五)分析蛋白质的亚细胞定位
利用WoLF PSORT(/)在线工具预测ZNF395蛋白定位于核内。
http://www.cbs.dtu.dk/services/ProtFun/
6、分析蛋白质的翻译后修饰:分析信号肽及其剪切位点: SignalIP http://www.cbs.dtu.dk/services/SignalP/;分析糖链连接点:分析O-连接糖蛋白, NetOGlyc,http://www.cbs.dtu.dk/services/NetOGlyc/;分析N-连接糖蛋白,NetNGlyc,http://www.cbs.dtu.dk/services/NetNGlyc/。
