DNAMAN软件中文说明书
序列分析软件DNAMAN 的使用方法简介

序列分析软件DNAMAN 的使用方法简介DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
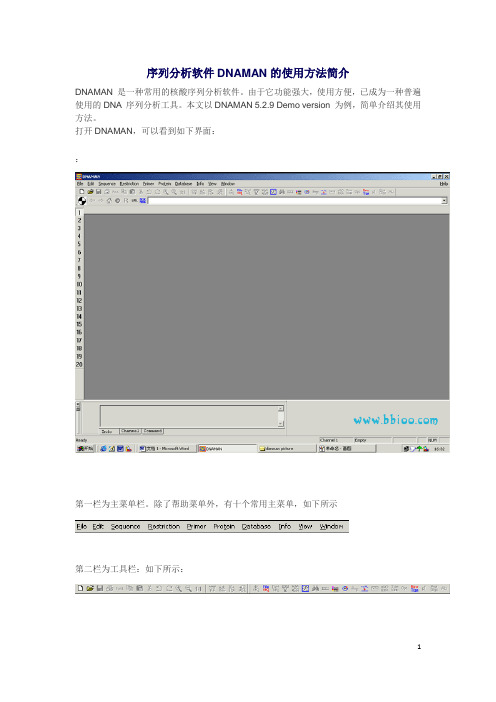
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
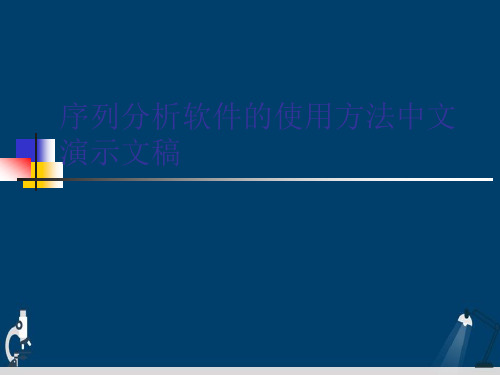
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
对话框选项说明如下:Sequence &Composition 显示序列和成分Reverse Complement Sequence 显示待分析序列的反向互补序列Reverse Sequence 显示待分析序列的反向序列Complement Sequence 显示待分析序列的互补序列Double Stranded Sequence 显示待分析序列的双链序列RNA Sequence 显示待分析序列的对应RNA 序列3.DNA 序列的限制性酶切位点分析将待分析的序列装入Channel,点击要分析的Channel,然后通过Restriction/Analysis 命令打开对话框,如下所示:参数说明如下:Results 分析结果显示其中包括:Show summary(显示概要) Show sites on sequence(在结果中显示酶切位点)Draw restriction map(显示限制性酶切图)Draw restriction pattern(显示限制性酶切模式图)Ignore enzymes with more than(忽略大于某设定值的酶切位点)Ignore enzymes with less than(忽略小于某设定值的酶切位点)Target DNA (目标DNA 特性)circular(环型DNA),dam/dcm methylation(dam/dcm 甲基化)all DNA in Sequence Channel(选择此项,在Sequence Channel 中的所有序列将被分析,如果选择了Draw restriction pattern,那么当所有的channel 中共有两条DNA 时,则只能选择两个酶分析,如果共有三个以上DNA 时,则只能用一个酶分析。
DNAman使用说明

查看文章DNAMAN使用说明书(中文)2008年04月16日星期三下午10:50DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
序列分析软件DNAMan
序列分析软件DNAMAN 的使用方法简介DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面::第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,如下所示第二栏为工具栏:如下所示:第三栏为浏览器栏:如下所示:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,如左所示:点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel ,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File|Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel(例如:channel5)来改变序列装入的Channel。
(2)通过Sequence|Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel。
可以通过Sequence|Current Sequence|Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence|Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
序列分析软件DNAMAN的使用方法

DNAMAN 是一种常用的核酸序列分析 软件。由于它功能强大,使用方便,已 成为一种普遍使用的DNA 序列分析工具。
打开DNAMAN,可以看到如下界面:
第一栏为主菜单栏。除了帮助菜单外,有十个 常用主菜单, 第二栏为工具栏: 第三栏为浏览器栏: 在浏览器栏下方的工作 区左侧,可见Channel 工具条,DNAMAN 提 供20 个Channel,点击Channel 工具条上相 应的数字,即可击活相应的Channel。 每个Channel 可以装入一个序列。将要分析 的序列(DNA 序列或氨基酸序列)放入 Channel 中可以节约存取序列时间,加快分 析速度。
Annotations 是否显示注释 Comparision 比对参数, 其中Window 代表Window size(单位比对长度), Mismatch 代表Mismatch size(单位比对长度中许 可的错配值)要快速比对,需将此项设为0。 Both stran 代表Both strand(双链比对)选择此项, 是指用Sequence 2 中的序列的正链和负链分别和 Sequence 1 比较。 Sequence 2 正链与Sequence 1 比较结果用黑色点 表示,Sequence 2 负链比对结果用红色点表示。
ห้องสมุดไป่ตู้
选择所需的项目,然后按提示操作点击按扭,出现下 列对话框: 参数说明如下: Enzyme 代表(enzyme data file),点击旁边的下拉按钮, 出现两个默认选项,restrict.enz 和dnamane.enz, 如果添加过自制的酶列表,则附加显示自制酶列表文 件名。 其中restrict.enz 数据文件包含180 种限制酶, dnamane.enz 数据文件包含2524 种限制酶。 选择其中一个数据文件,相应的酶在左边的显示框中 列出(按酶名称字母表顺序),鼠标双击酶名称,则 对应的酶被选中,在右边空白框中列出。
DNAMAN中文使用说明

DNAMAN中文使用说明好不容易找到了一个中文说明,希望可以帮助初学使用DNAMAN的朋友,更快的进入状态,当然现在网上也有汉化版的软件了,但是这个说明还是可以起到很好的帮助作用,与大家分享!DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
序列分析软件DNAMAN的使用方法中文演示文稿

序列分析软件DNAMAN的使用方法中文演示文稿第一部分:软件介绍1.DNAMAN是什么?-DNAMAN是一款用于DNA和蛋白质序列分析的软件。
-它提供多种功能,包括序列比对、引物设计、限制酶分析和进化树构建等。
2.DNAMAN的应用领域-DNAMAN广泛应用于生物学、生物技术和医药领域。
-它可以帮助研究人员进行序列分析、设计实验方案和解读实验结果。
第二部分:基本序列比对1.创建新项目-打开DNAMAN软件,点击“新建”按钮创建新项目。
-输入项目名称和序列信息,保存并打开该项目。
2.导入序列-点击“导入”按钮,选择需要比对的序列文件,点击“确定”导入。
-系统会自动将序列导入到项目中。
3.序列比对-选择需要比对的序列,点击“比对”按钮进行序列比对。
-系统会自动比对序列并生成比对结果。
4.结果解读-比对结果以图形和文本形式展示。
-可以通过选择不同的比对算法和调整参数来优化比对结果。
第三部分:引物设计1.创建新项目-打开DNAMAN软件,点击“新建”按钮创建新项目。
-输入项目名称和序列信息,保存并打开该项目。
2.导入标记序列-点击“导入”按钮,选择需要设计引物的标记序列文件,点击“确定”导入。
-系统会自动将标记序列导入到项目中。
3.引物设计-点击“引物设计”按钮,选择设计引物的参数和算法。
-系统会根据所选参数和算法自动生成引物设计结果。
4.结果解读-引物设计结果以图形和文本形式展示。
-可以通过选择不同的参数和算法来优化引物设计结果。
第四部分:限制酶分析1.创建新项目-打开DNAMAN软件,点击“新建”按钮创建新项目。
-输入项目名称和序列信息,保存并打开该项目。
2.导入限制酶序列-点击“导入”按钮,选择需要分析的限制酶序列文件,点击“确定”导入。
-系统会自动将限制酶序列导入到项目中。
3.限制酶分析-点击“限制酶分析”按钮,选择分析参数和算法。
-系统会根据所选参数和算法自动进行限制酶分析。
4.结果解读-限制酶分析结果以图形和文本形式展示。
DNAMAN的使用方法

文件菜单中选择“打开”或通过快捷键Ctrl+O,打开存储在计算机中的DNA序列文件。
保存文件
文件菜单中选择“保存”或通过快捷键Ctrl+S,将更改后的DNA序列存储到硬盘或其他存储设 备中。
文件格式要求
只支持常见的序列文件格式如FASTA、GenBank等,可以选择单个文件或批量导入。
D N A 序列的导入和编辑
分析序列统计学
序列长度分布
序列特征统计图
DNAMAN可以为所有序列生成序 列长度分布图,从而确定序列长 度最常见的地方,并且甚至可以 根据自己的喜好来更改分布参数。
这是用于比较DNA序列中各类特 征的常用工具。统计图通常是以 直方图的形式出现,幸运的是 DNAMAN可以自动生成这种统计 图并轻松进行定位和分析。
D N A 序列编辑
D N A 序列导入
D N A 序列统计信息
DNAMAN提供多种序列编辑工具, 例如添加碱基、删除碱基、反转 序列和互补序列等。
DNAMAN支持多种序列格式导入, 例如FASTA、GenBank等。
在编辑界面右侧的信息面板中, DNAMAN会自动生成序列的碱基 组成、止旋镇性能力等信息。
多样性分析
发现多样性和图形化分组模型对 于了解疾病的分布和传播至关重 要,DNAMAN通过比对分析大量 的DNA序列,可以进行多样性分 析并演示图形化分组模型。
D N A M A N 在植物和动物遗传学中的应用
BA C分析
通过资料库查询和选择BAC、 BIBAC、Cosmid等载体中的 DNA,进行序列分析和匹配 以获得目标DNA序列。
常见问题解答
1 D N A M A N 支持哪些文件格式?
便携式数据格式(PDF)、HTML网页、Microsoft Word和图像文件(PNG、JPEG、GIF)等。
DNAman使用方法

7.画质粒模式图
参数说明如下: Name : 要添加的酶切位点 的名称(例如HindIII) Position:位置(以碱基数表 示) 点击 Add Element选项,出 现如下对话框:
• Type :要素类型(共有三种类型, 鼠标点击即可切换) • (c)olor/Pattern: 填充色(共有 16种颜色供选择) • Name: 要素名称 • Start /End/Size:要素起点/终点/粗 细度 • 点击Add Text选项,出现如下对 话框:
6.PCR引物设计
点击 按钮,出现下列对话框: 选择选项,点击 按钮,出现:
7.画质粒模式图
• 我们常常要用到各种质粒图,无论是制作幻灯片,还是发 表文章,常常需要质粒图。DNAMAN 提供强大的绘质粒 图功能,能满足我们的需要。通过Restriction/Draw map 命令打开质粒绘图界面:
DNAMAN 使用方法
• 1.将待分析序列装入Channel
• • • • • •
2.以不同形式显示序列 3.DNA序列的限制性酶切位点分析 4.DNA序列比对分析 5.序列同源性分析 6. PCR引物设计 7.质粒模式图绘制
DNAMAN 使用方法
• DNAMAN是一种常用的核酸序列分析软件。由于它功能 强大,使用方便,已成为普遍使用的DNA序列分析工具。 以DNAMAN 5.2.9 Demo version为例,简单介绍其使用 方法。打开DNAMAN,可以看到如下界面:
• 输入要保存酶列表的文件名,点击 按钮即可保存。 自制酶列表可以方便分析特定的酶切位点。 • • Cutter 酶切识别序列长度;End 酶切产生的末端,其中 包括,Blunt(平头末端),5’Overhang(5’突出粘性末 端),3’Overhang(3’突出粘性末端),系统根据cutter和 end的设定情况,在左边酶列表中显示符合条件的酶。最后, 点击 按钮执行操作。
序列分析软件的使用方法中文演示文稿
Complement Sequence 显示待分析序列的 互补序列
Double Stranded Sequence 显示待分析序 列的双链序列
RNA Sequence 显示待分析序列的对应RNA 序列
3.DNA 序列的限制性酶切位点分析
说明如下: 如果要比对的序列在Channel 中,点击下拉箭头,选
择相应的Channel,则被选中的Channel 中的序列作 为参加比对的第一序列; 也可以从文件夹中选择参加比对的序列,在File 选择 框上点击即可。通过Length 选择参加比对的序列片 段。 Sequence 2 参加比对的第二序列选择框;选项说明 同上 Show Sequence 选择此项,当同源性大于设定值时, 将显示同源性;
区左侧,可见Channel 工具条,DNAMAN 提 供20 个Channel,点击Channel 工具条上相 应的数字,即可击活相应的Channel。 每个Channel 可以装入一个序列。将要分析 的序列(DNA 序列或氨基酸序列)放入 Channel 中可以节约存取序列时间,加快分 析速度。
要比较两个序列,可以使用DNAMAN 提供的序列比对工具Dot Matrix Comparision (点矩阵比较)通过 Sequense/Dot matrix comparision 命令打开比对界面,
点击对比界面左上角的按钮,出现下列 对话框:
参数说明如下:
Sequence type 序列类型 Sequence 1 参加比对的第一序列选择框,框内选项
参数说明如下:
Enzyme 代表(enzyme data file),点击旁边的下拉按钮,
出现两个默认选项,restrict.enz 和dnamane.enz, 如果添加过自制的酶列表,则附加显示自制酶列表文
序列分析软件DNAMAN 的使用方法简介

序列分析软件DNAMAN 的使用方法简介DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
对话框选项说明如下:Sequence &Composition 显示序列和成分Reverse Complement Sequence 显示待分析序列的反向互补序列Reverse Sequence 显示待分析序列的反向序列Complement Sequence 显示待分析序列的互补序列Double Stranded Sequence 显示待分析序列的双链序列RNA Sequence 显示待分析序列的对应RNA 序列3.DNA 序列的限制性酶切位点分析将待分析的序列装入Channel,点击要分析的Channel,然后通过Restriction/Analysis 命令打开对话框,如下所示:参数说明如下:Results 分析结果显示其中包括:Show summary(显示概要) Show sites on sequence(在结果中显示酶切位点)Draw restriction map(显示限制性酶切图)Draw restriction pattern(显示限制性酶切模式图)Ignore enzymes with more than(忽略大于某设定值的酶切位点)Ignore enzymes with less than(忽略小于某设定值的酶切位点)Target DNA (目标DNA 特性)circular(环型DNA),dam/dcm methylation(dam/dcm 甲基化)all DNA in Sequence Channel(选择此项,在Sequence Channel 中的所有序列将被分析,如果选择了Draw restriction pattern,那么当所有的channel 中共有两条DNA 时,则只能选择两个酶分析,如果共有三个以上DNA 时,则只能用一个酶分析。
分子生物学专业软件DNAMAN使用方法介绍
序列分析软件DNAMAN的使用方法简介吕惠平(新疆大学生命科学与技术学院;新疆生物资源基因工程重点实验室,乌鲁木齐,830046) DNAMAN是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA序列分析工具。
本文以DNAMAN 5.2.9 Demo version为例,简单介绍其使用方法。
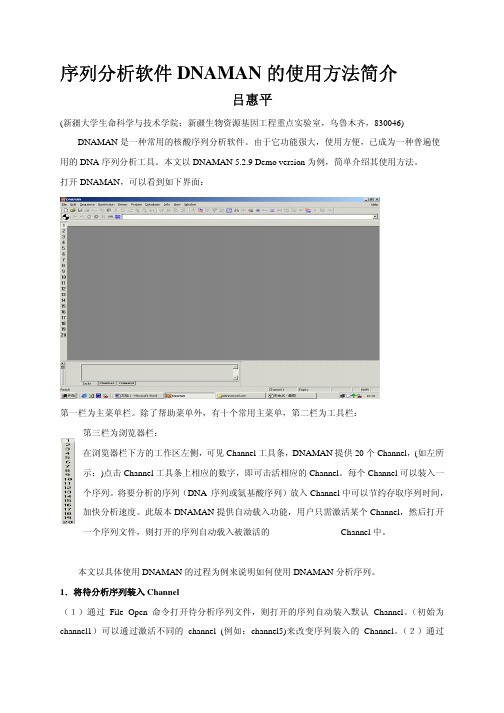
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel工具条,DNAMAN提供20个Channel,(如左所示:)点击Channel工具条上相应的数字,即可击活相应的Channel。
每个Channel可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel中可以节约存取序列时间,加快分析速度。
此版本DNAMAN提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的 Channel中。
本文以具体使用DNAMAN的过程为例来说明如何使用DNAMAN分析序列。
1.将待分析序列装入Channel(1)通过File Open命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence菜单的子菜单打开文件或将选定的部分序列装入Channel。
通过Sequence/Current Sequence/Analysis Defination命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
DNAMAN的使用方法

DNAMAN的使用方法第五章 DNAMAN 的使用方法DNAMAN是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA序列分析工具。
本文以DNAMAN 5.2.9 Demo version为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,如下所示:第二栏为工具栏:如下所示:第三栏为浏览器栏:如下所示:在浏览器栏下方的工作区左侧,可见Channel工具条,DNAMAN提供20个Channel,如左所示:点击Channel工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel中可以节约存取序列时间,加快分析速度。
此版本DNAMAN提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel中。
本文以具体使用DNAMAN的过程为例来说明如何使用DNAMAN分析序列。
1(将待分析序列装入Channel(,)通过File|Open命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为 channel1)可以通过激活不同的channel(例如:channel5)来改变序列默认装入的Channel。
(,)通过Sequence|Load Sequence菜单的子菜单打开文件或将选定的部分序列装入Channel。
如果只想分析序列的一部分,或者给待分析的序列添加批注,点击激活该序列所在的Channel,通过Sequence|Current Sequence|Analysis Defination命令打开一个对话框,如下所示:对话框选项说明如下:Name 序列名称Circular DNA 环形DNAStart pos 待分析序列起点End pos 待分析序列终点根据需要,可以设定上述选项的内容,如果要分析整个序列,可以点击按钮,如果当前序列不是DNA,则可点击按钮,如果要添加或修改批注,可以使用(添加),(移除),和(清除全部)三个按钮进行操作。
DNAMAN使用说明

DNAMAN使用说明书DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
对话框选项说明如下:Sequence &Composition 显示序列和成分Reverse Complement Sequence 显示待分析序列的反向互补序列Reverse Sequence 显示待分析序列的反向序列Complement Sequence 显示待分析序列的互补序列Double Stranded Sequence 显示待分析序列的双链序列RNA Sequence 显示待分析序列的对应RNA 序列3.DNA 序列的限制性酶切位点分析将待分析的序列装入Channel,点击要分析的Channel,然后通过Restriction/Analysis 命令打开对话框,如下所示:参数说明如下:Results 分析结果显示其中包括:Show summary(显示概要) Show sites on sequence(在结果中显示酶切位点)Draw restriction map(显示限制性酶切图)Draw restriction pattern (显示限制性酶切模式图)Ignore enzymes with more than(忽略大于某设定值的酶切位点)Ignore enzymes with less than(忽略小于某设定值的酶切位点)Target DNA (目标DNA 特性)circular(环型DNA),dam/dcm methylation(dam/dcm 甲基化)all DNA in Sequence Channel(选择此项,在Sequence Channel 中的所有序列将被分析,如果选择了Draw restriction pattern,那么当所有的channel 中共有两条DNA 时,则只能选择两个酶分析,如果共有三个以上DNA 时,则只能用一个酶分析。
序列分析软件DNAMan
序列分析软件DNAMAN的使用方法简介DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
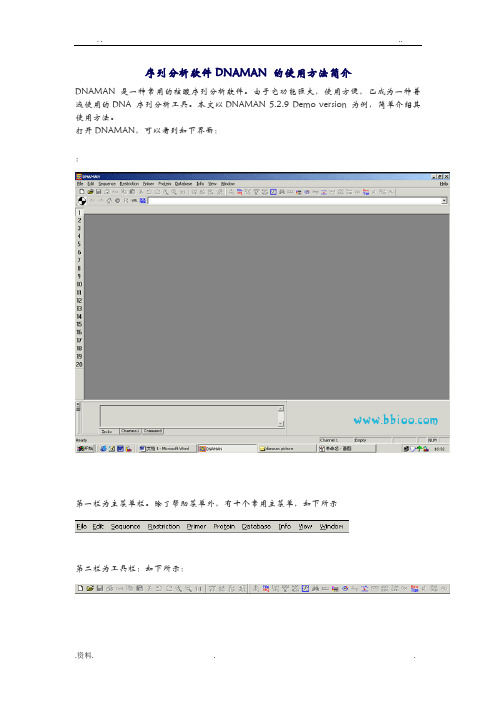
打开DNAMAN,可以看到如下界面::第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,如下所示第二栏为工具栏:如下所示:第三栏为浏览器栏:如下所示:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,如左所示:点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel ,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File|Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel(例如:channel5)来改变序列装入的Channel。
(2)通过Sequence|Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel。
可以通过Sequence|Current Sequence|Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence|Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
DNAman使用方法

按扭, 按扭,出现
Enzyme :代表 代表enzyme data file,点击旁边的下拉按钮,出现两个默认选项 ,点击旁边的下拉按钮, ,restrict.enz和dnamane.enz,如果添加过自制的酶列表,则附加显示自制 和 ,如果添加过自制的酶列表, 酶列表文件名。其中restrict.enz数据文件包含 种限制酶,dnamane.enz 数据文件包含180种限制酶 种限制酶, 酶列表文件名。其中 数据文件包含 数据文件包含2524种限制酶。选择其中一个数据文件,相应的酶在左边的 种限制酶。 数据文件包含 种限制酶 选择其中一个数据文件, 显示框中列出(按酶名称字母表顺序),鼠标双击酶名称, ),鼠标双击酶名称 显示框中列出(按酶名称字母表顺序),鼠标双击酶名称,则对应的酶被 选中,在右边空白框中列出。要自制酶切列表, 选中,在右边空白框中列出。要自制酶切列表,可以从左边酶列表中双击 鼠标选择多种酶(例如puc18 multiple cloning sites),然后点击 ),然后点击 鼠标选择多种酶(例如 ), 按 钮出现下列对话框: 钮出现下列对话框:
5.序列同源性分析 .
(1)两序列同源性分析 ) 通过Sequence/Two Sequence Alignment命令打开对话框,如 命令打开对话框, 通过 命令打开对话框 下所示: 下所示: 参数说明如下: Alignment method :比对方法, 通常可选Quick(快速比对)或 Smith&Waterman(最佳比对),当 选择快速比对时,设置较小的ktuple值,可以提高精确度,当序 列较长时,一般要设置较大的ktuple值(DNA序列:k-tuple值可选范 序列: 序列 值可选范
序列分析软件DNAMan

序列分析软件DNAMAN 的使用方法简介DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面::第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,如下所示第二栏为工具栏:如下所示:第三栏为浏览器栏:如下所示:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,如左所示:点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel ,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File|Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel(例如:channel5)来改变序列装入的Channel。
(2)通过Sequence|Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel。
可以通过Sequence|Current Sequence|Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence|Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
DNAMAN软件中文说明书

DNAMAN软件中文说明书DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
对话框选项说明如下:Sequence &Composition 显示序列和成分Reverse Complement Sequence 显示待分析序列的反向互补序列Reverse Sequence 显示待分析序列的反向序列Complement Sequence 显示待分析序列的互补序列Double Stranded Sequence 显示待分析序列的双链序列RNA Sequence 显示待分析序列的对应RNA 序列3.DNA 序列的限制性酶切位点分析将待分析的序列装入Channel,点击要分析的Channel,然后通过Restriction/Analysis 命令打开对话框,如下所示:参数说明如下:Results 分析结果显示其中包括:Show summary(显示概要)Show sites on sequence(在结果中显示酶切位点)Draw restriction map(显示限制性酶切图)Draw restriction pattern(显示限制性酶切模式图)Ignore enzymes with more than(忽略大于某设定值的酶切位点)Ignore enzymes with less than(忽略小于某设定值的酶切位点)Target DNA (目标DNA 特性)circular(环型DNA),dam/dcm methylation(dam/dcm 甲基化)all DNA in Sequence Channel(选择此项,在Sequence Channel 中的所有序列将被分析,如果选择了Draw restriction pattern,那么当所有的channel 中共有两条DNA 时,则只能选择两个酶分析,如果共有三个以上DNA 时,则只能用一个酶分析。
- 1、下载文档前请自行甄别文档内容的完整性,平台不提供额外的编辑、内容补充、找答案等附加服务。
- 2、"仅部分预览"的文档,不可在线预览部分如存在完整性等问题,可反馈申请退款(可完整预览的文档不适用该条件!)。
- 3、如文档侵犯您的权益,请联系客服反馈,我们会尽快为您处理(人工客服工作时间:9:00-18:30)。
DNAMAN软件中文说明书DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
对话框选项说明如下:Sequence &Composition 显示序列和成分Reverse Complement Sequence 显示待分析序列的反向互补序列Reverse Sequence 显示待分析序列的反向序列Complement Sequence 显示待分析序列的互补序列Double Stranded Sequence 显示待分析序列的双链序列RNA Sequence 显示待分析序列的对应RNA 序列3.DNA 序列的限制性酶切位点分析将待分析的序列装入Channel,点击要分析的Channel,然后通过Restriction/Analysis 命令打开对话框,如下所示:参数说明如下:Results 分析结果显示其中包括:Show summary(显示概要)Show sites on sequence(在结果中显示酶切位点)Draw restriction map(显示限制性酶切图)Draw restriction pattern(显示限制性酶切模式图)Ignore enzymes with more than(忽略大于某设定值的酶切位点)Ignore enzymes with less than(忽略小于某设定值的酶切位点)Target DNA (目标DNA 特性)circular(环型DNA),dam/dcm methylation(dam/dcm 甲基化)all DNA in Sequence Channel(选择此项,在Sequence Channel 中的所有序列将被分析,如果选择了Draw restriction pattern,那么当所有的channel 中共有两条DNA 时,则只能选择两个酶分析,如果共有三个以上DNA 时,则只能用一个酶分析。
选择所需的项目,然后按提示操作点击按扭,出现下列对话框:参数说明如下:Enzyme代表(enzyme data file),点击旁边的下拉按钮,出现两个默认选项,restrict.enz 和dnamane.enz,如果添加过自制的酶列表,则附加显示自制酶列表文件名。
其中restrict.enz 数据文件包含180 种限制酶,dnamane.enz 数据文件包含2524 种限制酶。
选择其中一个数据文件,相应的酶在左边的显示框中列出(按酶名称字母表顺序),鼠标双击酶名称,则对应的酶被选中,在右边空白框中列出。
要自制酶切列表,可以从左边酶列表中双击鼠标选择多种酶(例如puc18 multiple cloning sites),然后点击按钮出现下列对话框:输入要保存酶列表的文件名,点击按钮即可保存。
自制酶列表可以方便分析特定的酶切位点。
Cutter 酶切识别序列长度;End 酶切产生的末端,其中包括,Blunt(平头末端),5’Overhang(5’突出粘性末端),3’Overhang(3’突出粘性末端),系统根据cutter 和end 的设定情况,在左边酶列表中显示符合条件的酶。
最后,点击按钮执行操作。
4.DNA 序列比对分析(Dot Matrix Comparision)要比较两个序列,可以使用DNAMAN 提供的序列比对工具Dot Matrix Comparision (点矩阵比较)通过Sequense/Dot matrix comparision 命令打开比对界面,如下图:点击对比界面左上角的按钮,出现下列对话框:参数说明如下:Sequence type 序列类型Sequence 1 参加比对的第一序列选择框,框内选项说明如下:如果要比对的序列在Channel 中,点击下拉箭头,选择相应的Channel,则被选中的Channel 中的序列作为参加比对的第一序列;也可以从文件夹中选择参加比对的序列,在File 选择框上点击即可。
通过Length 选择参加比对的序列片段。
Sequence 2 参加比对的第二序列选择框;选项说明同上Show Sequence 选择此项,当同源性大于设定值时,将显示同源性;(此功能未见)Annotations 是否显示注释Comparision 比对参数,其中Window 代表Window size(单位比对长度),Mismatch 代表Mismatch size(单位比对长度中许可的错配值)要快速比对,需将此项设为0。
Both stran 代表Both strand(双链比对)选择此项,是指用Sequence 2 中的序列的正链和负链分别和Sequence 1 比较。
Sequence 2 正链与Sequence 1 比较结果用黑色点表示,Sequence 2 负链比对结果用红色点表示。
Plot box 点阵图表显示参数,Position(起点坐标)Width(宽度值)Height(高度值)Frame size(边框线粗度值)Dot size(点粗度值)Gridline(虚线框数)。
参数设定好后,点击按钮执行操作。
5.序列同源性分析(1)两序列同源性分析通过Sequence/Two Sequence Alignment 命令打开对话框,如下所示:参数说明如下:Alignment method 比对方法,通常可选Quick(快速比对)或Smith&Waterman(最佳比对),当选择快速比对时,设置较小的k-tuple 值,可以提高精确度,当序列较长时,一般要设置较大的k-tuple 值。
(dna序列:k-tuple 值可选范围2—6;蛋白质序列:k-tuple 值可选范围1—3。
其它参数说明从略。
(2)多序列同源性分析通过打开Sequence/Multiple Sequence Alignment 命令打开对话框,如下所示:参数说明如下:File 从文件中选择参加比对的序列Folder 从文件夹中选择参加比对的序列Channel 从channel 中选择参加比对的序列Dbase 从数据库中选择参加比对的序列Remove 清除选择的序列(鼠标点击左边显示框中的序列名选择)Clear 清除全部序列点击按钮,出现方法选择对话框:选择其中一种方法,点击按钮,出现下列对话框:如果在前一对话框选择的是Fast alignment,则在此对话框中选择Quick alignment,否则选择Dynamic alignment 即可。
其它参数不必改变,点击对话框中间的使其它参数取原始默认值。
点击按钮,出现下列对话框:点击对话框中间的,然后点击执行操作。
结果如下所示:点击左上角按钮,可以从弹出的对话框中选择不同的结果显示特性选项。
点击按钮下的按钮,出现下列选择项:可以通过这些选项,绘制同源关系图(例如Tree/homology tree 命令)。
显示蛋白质二级结构(ProteinSecondary Structure 命令),绘制限制性酶切图(Restriction Analysis 命令)等。
同源关系图举例如下:(Tree/Homology Tree 命令)6.PCR 引物设计首先,将目标DNA 片段装入Channel,并激活Channel。
点击主菜单栏中的Primer 主菜单,出现下拉菜单,如下所示:点击Design PCR Primers for DNA 命令,出现下列对话框:参数说明如下:Primer locations on target 引物定位其中包括下列选项:Product size(扩增目的片段大小)Sense primer (正向引物选择区)Antisense primer(反向引物选择区)Primer 引物特性包括Length(引物长度),Tm 值, GC 含量等参数;Reject primer 引物过滤(将符合引物过滤条件的引物过滤掉)包括下列选项:3’dimer(可形成3’端自我互补的碱基数)Hairpin stem(可形成发卡颈环结构的碱基数)PolyN(多聚碱基)3’Uique(3’端严格配对碱基数)Primer-Primer(含义未知)All matches(引物互补配对百分数)Consentrations 浓度设定Product for hybridyzat(ion)PCR 产物用于Southern Blot 探针杂交点击按钮,出现下列对话框:.选择需要的选项,点击按钮,出现:点击按钮,完成操作。
7.画质粒模式图我们常常要用到各种质粒图,无论是制作幻灯片,还是发表文章,常常需要质粒图。
DNAMAN 提供强大的绘质粒图功能,能满足我们的需要。
通过Restriction/Draw map 命令打开质粒绘图界面:将鼠标移动到圆圈上,等鼠标变形成“I”时,单击鼠标左键,出现如下菜单:菜单说明如下:Position 当前位置Add Site 添加酶切位点Add Element 添加要素Add Text 添加文字Insert Fragment 插入片断Copy Fragment 复制片断Cut Fragment 剪切片断Remove Fragment 清除片断Frame Thickness 边框线粗细调节点击Add Site 选项,出现如下对话框:参数说明如下:Name 要添加的酶切位点的名称(例如HindIII)Position 位置(以碱基数表示)点击Add Element 选项,出现如下对话框:参数说明如下:Type 要素类型(共有三种类型,鼠标点击即可切换)(c)olor/Pattern 填充色(共有16 种颜色供选择)Name 要素名称Start /End/Size 要素起点/终点/粗细度点击Add Text 选项,出现如下对话框:输入要添加的文字,点击Font 按钮设置字体和格式,选择Horizontal(水平显示)或Vertical(垂直显示),点击按钮即可。
