怎样查找一个基因的启动子区域
确定启动子位置的方法(一)

确定启动子位置的方法(一)确定启动子位置引言启动子是指基因的一个特殊区域,它在基因转录过程中起着重要的作用。
确定启动子位置是基因组学研究中的一项重要任务,对于深入理解基因的调控机制有着非常重要的意义。
本文将介绍几种常见的方法来确定启动子位置。
1.实验方法5’ RACE5’ RACE (Rapid Amplification of cDNA Ends) 是一种常用的实验方法,用于确定基因的启动子位置。
该方法通过引物扩增方法,在未知启动子区域的5’端合成一条cDNA链,并通过PCR扩增获得启动子序列。
5’ RACE在启动子区域进行测序,可获得启动子的精确位置。
Chromatin Immunoprecipitation (ChIP)ChIP是一种通过抗体和染色质上的特定蛋白结合来确定启动子位置的方法。
该方法首先通过交联和剪切处理来固定染色质上的蛋白质-DNA复合物,然后使用特定的抗体来免疫沉淀(IP)所要分析的蛋白质,最后通过PCR或测序来检测与启动子相关的DNA序列。
2.计算方法基于序列保守性的方法基于序列保守性的方法通过比对物种间的基因组序列来确定启动子位置。
这种方法假设启动子处的序列在不同物种间具有高度的保守性,因此可以通过比对序列中的保守区域来确定启动子的位置。
基于转录因子结合位点的方法许多转录因子结合在启动子区域,因此基于转录因子结合位点的方法可以帮助确定启动子位置。
通过分析转录因子结合位点的分布情况,并结合表观遗传学修饰等信息,可以预测启动子的位置。
基于表达谱和转录本结构的方法基于表达谱和转录本结构的方法可以通过分析基因的表达谱和转录本结构来确定启动子位置。
这种方法假设在基因的表达谱和转录本结构中存在着与启动子相关的特征,通过分析这些特征可以推断出启动子的位置。
总结确定启动子位置是基因组学研究中的一项重要任务。
本文介绍了几种常见的方法,包括实验方法和计算方法。
实验方法包括5’ RACE 和ChIP等,而计算方法则包括基于序列保守性、转录因子结合位点和表达谱转录本结构等方法。
干货7个步骤教你找到启动子

干货7个步骤教你找到启动子
作者:解螺旋·子非鱼
如需转载请注明来源:解螺旋·医生科研助手
导语
看到一大串密码一样的序列,要怎么找出启动子呢?其实很简单,也就7步,跟着小鱼做就行。
师弟对着电脑上的一大串序列发呆,小鱼问道,“师弟,你这是在格物致知吗?”
“没有啦,我在想怎么把这个基因启动子找出来。
”
“试试用Map viewer吧!”
下面小鱼就以人的K-RAS基因为例讲述一下找基因启动子序列的具体操作步骤:
1.打开NCBI的Map viewer页面,
/mapview/index.html
2.点击“GO”出现如下页面:
3.出现下图,RAS参考序列给出了两个,序列有微小的差异,但总体来说基本相同。
现在普遍采用的是“reference”那个序列。
4.点击上述两条序列第一条序列(即12 reference)对应的“Genes seq”,出现新的页面,点击下图出现的“Download/ViewSequence/Evidence ”,即可下载查看序列等功能。
5.出现的页面提示K-ras基因在染色体上的位置:
6.因为启动子一般在-2000~+200区域,把页面中的参数修改一下:
7.那么就得到K-ras的启动子区域,如下图:。
一文教会你查找基因的启动子、UTR、TSS等区域以及预测转录因子结合位点

一文教会你查找基因的启动子、UTR、TSS等区域以及预测转录因子结合位点基础知识首先我们了解一些基础知识(注:文中图片皆可点击放大查看!):启动子(promoter):与RNA聚合酶结合并能起始mRNA合成的序列。
做生信分析时,一般选择上游1 kb,下游 500 nt,也有选上下游各1 kb的。
如果关注核心启动子,可见生信宝典之前发布的Jaspar数据库介绍。
获取正链或负链的启动子序列时要注意方向。
之前awk的教程中有些提及。
转录起始点(TSS):转录时,mRNA链第一个核苷酸相对应DNA链上的碱基,通常为一个嘌呤。
UTR(Untranslated Regions):即非翻译区,是信使RNA (mRNA)分子编码区(CDS)两端的非编码片段。
5’-UTR从mRNA起点的甲基化鸟嘌呤核苷酸帽延伸至AUG起始密码子,3’-UTR从编码区末端的终止密码子延伸至多聚A尾巴(Poly-A)的末端。
生信老司机以中心法则为主线讲解组学技术的应用和生信分析心得- 限时免费中讲述了如何基于高通量数据对这些区域的调节变化进行分析,可配合此文观看。
1. 查找基因的启动子区域-NCBI1. 打开PubMed:/pubmed2. 选择Gene,输入IL17A,点击search,结果如下图,点击第一个:3. 下拉到下图位置,可以看到该基因的以下信息:点击Tools,选择Sequence Text View:还可以看到如下序列信息:4. 以上只是该基因的一些信息,可以用于查找相应的UTR等区域,下面进入正题,寻找promoter区域。
还是拉到如下图位置,点击FASTA:5. 基因位置信息如下图:6. 一般认为基因上游2 kb区域为该基因的promoter区域,所以将基因上游2 kb序列调出来:7. 复制上述序列就是基因的启动子序列了。
2. 查找基因的启动子区域-UCSC1. 打开UCSC:/,点击Table Browser:2. 按照下图所示填好基因相关信息,点击get output:3.选择genomic:4. 勾选Promoter/Upstream by选项,并将其改为2000 bases,然后点击get sequence:5. 得到下面的序列信息,开头直到第一个大写字母前面的所有小写字母序列即为该基因的promoter序列,你可以跟NCBI上得到的序列比对一下,看看是不是一样的呢?3. 转录因子结合位点的预测1.后面的预测步骤是改版前的Jaspar,可见上一篇介绍Jaspar的文章学习在新版Jaspar中怎么预测启动子区域的转录因子结合位点。
如何找一个基因的启动子序列呢

如何找一个基因的启动子序列呢一个基因的启动子序列是一个基因组区域,位于基因的上游,并能够识别和结合转录因子,调控基因的转录活性。
寻找一个基因的启动子序列可以通过多种方法和技术来进行。
1. 基因组数据挖掘:最简单的方法是使用公开的基因组数据库,例如Ensembl、NCBI等,使用基因名或序列信息目标基因,并获取其序列信息。
这些数据库通常会提供基因的起始位置和上游区域的信息。
2.序列比对和多序列比较:如果基因组数据库中没有目标基因的启动子序列信息,可以通过对已知相关物种的基因组进行序列比对来获取启动子序列。
过去研究或其他相关文献中可能已经报道了该基因位点的启动子信息,可以通过多序列比较来找到高度保守的区域进行分析。
3.实验方法:寻找基因的启动子序列也可以通过实验方法来进行。
以下是几个常用的实验方法:-基因克隆:通过PCR扩增目标基因的上游区域,然后将PCR产物克隆到适当的载体中进行测序。
从测序结果中截取相应的序列作为启动子序列。
- 5' RACE(Rapid Amplification of cDNA Ends):通过5' RACE技术,可以找到目标基因的转录起始位点,从而确定启动子序列。
这种方法从mRNA上游端引导逆转录聚合酶链式反应(RT-PCR),然后再通过测序获取启动子序列。
-转录组学方法:RNA测序和转录组学方法可以检测到基因的转录产物,从而很大程度上能够帮助确定启动子序列。
RNA测序可以生成从基因的5'端到3'端的转录产物的序列信息,因此可以利用这些数据来识别基因的启动子区域。
4. 计算方法:计算方法可以利用一些生物学特征或机器学习算法来预测基因的启动子序列。
例如,启动子序列通常富含一些特定的DNA序列模式,如TATA box、CAAT box和GC box等。
利用这些DNA序列模式的分布和相互作用关系,可以预测和确定基因的启动子区域。
在寻找基因的启动子序列时,需要根据研究目的选择适当的方法。
如何找一个基因的启动子序列呢?
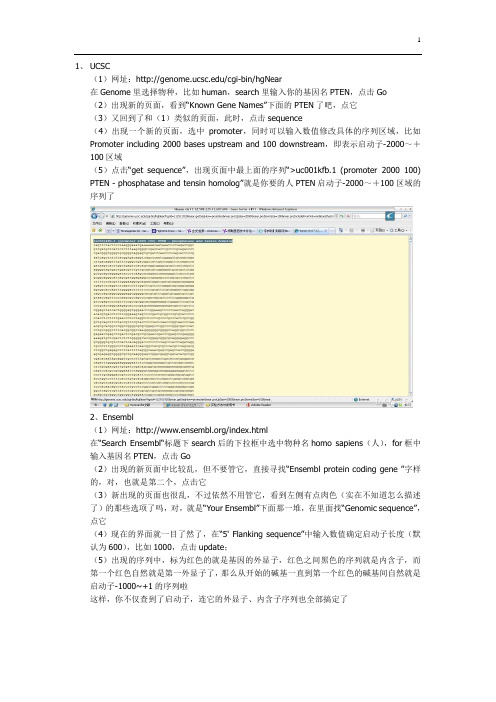
1、UCSC(1)网址:/cgi-bin/hgNear在Genome里选择物种,比如human,search里输入你的基因名PTEN,点击Go(2)出现新的页面,看到“Known Gene Names”下面的PTEN了吧,点它(3)又回到了和(1)类似的页面,此时,点击sequence(4)出现一个新的页面,选中promoter,同时可以输入数值修改具体的序列区域,比如Promoter including 2000 bases upstream and 100 downstream,即表示启动子-2000~+100区域(5)点击“get sequence”,出现页面中最上面的序列“>uc001kfb.1 (promoter 2000 100) PTEN - phosphatase and tensin homolog”就是你要的人PTEN启动子-2000~+100区域的序列了2、Ensembl(1)网址:/index.html在“Search Ensembl“标题下search后的下拉框中选中物种名homo sapiens(人),for框中输入基因名PTEN,点击Go(2)出现的新页面中比较乱,但不要管它,直接寻找“Ensembl protein coding gene ”字样的,对,也就是第二个,点击它(3)新出现的页面也很乱,不过依然不用管它,看到左侧有点肉色(实在不知道怎么描述了)的那些选项了吗,对,就是“Your Ensembl”下面那一堆,在里面找“Genomic sequence”,点它(4)现在的界面就一目了然了,在“5' Flanking sequence”中输入数值确定启动子长度(默认为600),比如1000,点击update;(5)出现的序列中,标为红色的就是基因的外显子,红色之间黑色的序列就是内含子,而第一个红色自然就是第一外显子了,那么从开始的碱基一直到第一个红色的碱基间自然就是启动子-1000~+1的序列啦这样,你不仅查到了启动子,连它的外显子、内含子序列也全部搞定了3、SIB-EPD(1)网址:http://www.epd.isb-sib.ch/(2)具体使用方法大同小异,就是输入物种名、基因名,限定启动子序列区域不过有了前两个,我想已经足够用了,个人感觉SIB-EPD的库容量太小,很多基因查不到我以前回的贴,总结一下ensembl一般也和NCBI的一致,你的情况可能例外。
使用UCSC查找基因启动子区域方法

应用UCSC查找基因启动子(promoter)、内含子、外显子序列(2015)本文原文来源于网络,因网站相关网页有所变化,特改写原文,望对同同仁有所帮助。
启动子的甲基化,转录因子与启动子的结合调控基因的表达等研究领域一直较为热门。
本文图文形式讲解了启动子的概念,利用UCSC如何查找一个基因的启动子序列,以及外显子和内含子序列的显示。
在讲述某个基因的启动子查询之间,我们有必要对基础知识进行一下复习和总结。
先看一下中心法则:启动子是在DNA转录为RNA这一步过程中发挥作用的,在此要与DNA自身复制起始点(称作复制子)和由mRNA翻译为蛋白质时的翻译起始点(以起始密码子ATG为标志)区别开来。
定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
启动子是RNA聚合酶特异性识别和结合的部位。
启动子方向性,位于转录起始点上游,本身并不被转录。
DNA链上与RNA链的第一个核苷酸对应的碱基标记为+1(如下图),由此碱基向上游(5’端)数的碱基顺序数为负(-1,-2,……),向下游(3’端)数的碱基为正(+2,+3,……)区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
总结起来,也就是说启动子约在与mRNA所对应的DNA序列之前约2000个左右的碱基。
明白了启动子的含义之后,我们以人(Human)的NDRG4(N-MycDownstream- Regulated Gene 4)为例,应用UCSC基因组浏览器开始查找该基因的启动子序列。
网址/index.html。
进入UCSC的主页后,在其左侧(如上图)点击第一项GenomeBrowser,进入基因组浏览器入口,如下图按照上图中的下拉选项,选择Mammal下的Human,assembly选择最新,search term 处填写需要查找的基因名称。
如何查找一个基因的启动子序列

如何查找一个基因的启动子序列发表者:刘小丰 (访问人次:6102)刘小丰收集整理定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
这项搜寻要从UCSC基因组浏览器开始,网址为/cgi-bin/hgGateway。
以编码pendrin (PDS)的基因为例来说明上述问题。
PDS与耳蜗的异常发育、感觉神经性听力下降以及弥散性甲状腺增大(甲状腺肿)有关。
进入UCSC的主页后,在Organism的下拉菜单中选择Human,然后点击Browser。
使用者现在到了人类基因组浏览器入口。
本例的搜寻很简单:在assembly的下拉菜单中选择Dec. 2001,在position框中键入pendrin,然后点击Submit。
返回的页面结果显示一个已知的基因和两个mRNA序列。
继续点击mRNA序列的登录号AF030880,出现包含这个mRNA区域的图解概要。
为了获得这个区域更清晰的图像,点击紧靠zoom out的1.5X按钮。
最后点击页面中部的reset all按钮,使各个路径的设置恢复默认状态。
然而,对于本例的搜寻目的来说,默认设置不是理想的设置。
按照视图利用页面底部的Track Controls按纽,将一些路径设置为hide模式(即不显示),其他设置为dense模式(所有资料密集在一条直线上);另一些路径设置为full模式(每个特征有一个分开的线条,最多达300)。
在考虑这些路径内究竟存在那些资料之前,对这些路径的内容和表现做一个简要的讨论是必要的,许多这些讨论是由外界提供给UCSC的。
下面是对基因预测方法的更进一步讨论,这些信息也可以在其他地方找到。
NCBI查基因 编码区 启动子区 外显子
问题:NCBI中怎样查找编码区/非编码区、起始密码子、启动子、外显子/内含子。
启动子
一般定义启动子,都是upstream 1000bp,downstream1000bp的那段序列。
或者根据你的实验。
你去ensemble,输入基因,找到exon,点开,在configuration里面选好flank多少bp 的序列,选好之后自动刷新,就出来了。
在序列里面,ensemble用不同的颜色标出来不同区域,5‘UTR之类的,还有exon,intron,转录起始位点等等,flank的区域就是你选的promoter 了。
开放阅读框
在分子生物学中,开放阅读框(Open Reading Frame, ORF)从起始密码子开始,是DNA序列中具有编码蛋白质潜能,一段无终止密码子打断的碱基序列。
寻找启动子区域和预测转录因子结合位点

寻找promoter区域
小写字母为promoter区域
大写字母为基因区域,与NCBI结果相 同
ATG为CDS区起始密码子
10
寻找promoter区域
/index.html 选择human 输入 ankh 选择Gene,点击 GeneID ENSG00000154122 点击左边的Export data
输入14871887到14873886 )
6
寻找promoter区域
/ 选择genomes 在clade选择Mammal,genome选择Human,assmebly选择最新的数据库,gene中输入ANKH 点击Tables 在track中选择RefSeq Genes,在output format中选择sequence 点击get output。 选择genomic。
复制白底黑色区域即为promoter区域。
白底黑字 为启动子
区域
紫底黑字 为基因区
域
粉底黑字为编 码区,ATG为
启示密码子
5
寻找promoter区域
在前两张幻灯片中选择FASTA 在右边Change region shown输入14871887到14873887 Display options选择Show reverse complement 可以直接得到FASTA格式的promoter核苷酸序列(似omoter区域
5 Flanking sequence 输入2000 Options for FASTA sequence中Genomic选5 Flanking sequence, deselect all 点击Next(不管正反此法都适用)
12
寻找promoter区域
如何查找基因的启动子区

如何查找一个基因的启动子序列定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
这项搜寻要从UCSC基因组浏览器开始,网址为/。
以编码pendrin (PDS)的基因为例来说明上述问题。
PDS与耳蜗的异常发育、感觉神经性听力下降以及弥散性甲状腺增大(甲状腺肿)有关。
进入UCSC的主页后,在Organism的下拉菜单中选择Human,然后点击Browser。
使用者现在到了人类基因组浏览器入口。
本例的搜寻很简单:在assembly的下拉菜单中选择Dec. 2001,在position 框中键入pendrin,然后点击Submit。
返回的页面结果显示一个已知的基因和两个mRNA序列。
继续点击mRNA序列的登录号AF030880,出现包含这个mRNA区域的图解概要。
为了获得这个区域更清晰的图像,点击紧靠zoom out的1.5X按钮。
最后点击页面中部的reset all按钮,使各个路径的设置恢复默认状态。
然而,对于本例的搜寻目的来说,默认设置不是理想的设置。
按照视图利用页面底部的Track Controls 按纽,将一些路径设置为hide模式(即不显示),其他设置为dense模式(所有资料密集在一条直线上);另一些路径设置为full模式(每个特征有一个分开的线条,最多达300)。
在考虑这些路径内究竟存在那些资料之前,对这些路径的内容和表现做一个简要的讨论是必要的,许多这些讨论是由外界提供给UCSC 的。
下面是对基因预测方法的更进一步讨论,这些信息也可以在其他地方找到。
对于Known Genes(已知基因)和预测的基因路径来说,一般的惯例是以一个高的垂直线或块状表示每个编码外显子,以短的垂直线或块状表示5′端和3′端非翻译区。
在UCSC查找可能的启动子

在UCSC查找可能的启动子1、进入网站/index.html。
2、点击Tables菜单,在position后面的搜索框内写入待查的基因名称,点击getoutput。
3、出现一系列候选序列。
当搜索用词不特异的时候会出来太多的结果,只显示500条。
4、点击自己目的基因的结果链接,会出现该基因在染色体上的位置 (有时候会直接跳到选择genome,protein,mRNA那一页面,可能是在搜索词比较特异的情况写),继续getoutput。
5、选择genome这一项。
6、promoter/up stream前面的框中打勾,一般的启动子长度大约为2kb左右,这个数字可以修改。
为便于观察,可继续修改下面的几个选项。
这里选择CDS大写。
7、点击get sequence即可得到结果。
UTR和upstream是分开的,CDS是大写的,可以看到起始码。
copyATG以前的序列进行启动子分析。
pcr以genome为模板。
在Ensembl查找可能的启动子1、进入网站/index.html,选择物种,填入搜索的基因名称。
2、出来2个结果。
本例中貌似是同一个。
点击相应链接进入新页面。
3、貌似有2个不同的转录本。
点击Exon Info。
4、新页面中即可看到5' upstreamsequence。
可以在Flanking sequence at either end oftranscript后面的框中修改期望显示的序列长度。
一般启动子最好选>2kb。
然后copy所显示的上游序列进行分析。
如何查找基因的启动子区

如何查找基因的启动子区基因的启动子区是基因的调控区域,其位于基因的上游区域。
启动子区域的特点是具有包括启动子、增强子、转录因子结合位点等在内的一系列调控元件,这些元件共同参与了基因的转录调控。
找到一个基因的启动子区,可以帮助我们理解基因的调控机制,进而揭示基因功能和可能的突变带来的影响。
下面将介绍几种常用的方法来查找基因的启动子区。
1.基于生物信息学的预测方法:在基因组学研究中,有很多基于生物信息学的预测方法可以用来查找启动子区域。
这些方法的基本原理是通过分析DNA序列中的一些保守模体和序列特征来预测潜在的启动子区域。
常用的生物信息学工具有TSSGuru、PromoterInspector、Softberry和PromoterScan等,这些工具常常依赖于一些已知的和保守的启动子模体来进行预测。
2.实验室方法:实验室方法一般用于鉴定启动子区域的转录起始位点(TSS)。
这些方法包括实验室测定的转录起始位点显示法(5'-RACE)和转录起始位点定位法(TSS mapping)。
5'-RACE利用了RNA反转录和PCR扩增的原理,可以将对应于转录起始位点的RNA序列扩增出来,并通过测序鉴定转录起始位点。
TSS mapping是一种高通量测定转录起始位点的方法,它可以通过酶切或测序技术鉴定转录起始位点。
3.基于转录因子结合的方法:转录因子是调控基因表达的关键分子,它们结合到基因的启动子区域上,并激活或抑制基因的转录。
通过研究转录因子的结合位点可以找到潜在的启动子区域。
常用的方法有DNA亲和层析法(DNA affinitychromatography)、ChIP-Seq和DNase-seq等。
其中,ChIP-Seq是一种高通量的方法,可以通过将转录因子与其结合DNA片段一起进行测序,从而确定转录因子结合位点和相关启动子区域。
4.跨物种比较法:在物种间比较的基础上查找启动子区域是一种常用的方法。
查找启动子区

寻找promoter区域
• 出现一系列候选序列。当搜索用词不特异的时候会出来太多的结果,只显示500条。
寻找promoter区域
• 点击自己目的基因的结果链接,会出现该基因在染色体上的位置 (有时候会直接跳到 选择genome,protein,mRNA那一页面,可能是在搜索词比较特异的情况写),
直线或块状表示每个编码外显子,以短的垂直线或块状表示5′端和3′端非翻译区。起连 接作用的内含子以非常细的线条表示。翻译的方向由沿着细线的箭头指示。
寻找promoter区域
• 本例的搜寻目的来说,默认设置不是理想的设置。 • 按照视图利用页面底部的Track Controls按钮,将一些路径设置为hide模式(即不显
寻找promoter区域
• 找到所需要的gene,点击 • 出来2个结果。本例中貌似是同一个。点击相应链接进入新页面。
寻找promoter区域
• 貌似有2个不同的转录本。点击Exon Info。
寻找promoter区域
• 新页面中即可看到5' upstream sequence。可以在Flanking sequence at either end of transcript后面的框中修改期望显示的序列长度。一般启动子最 好选>2kb。然后copy所显示的上游序列进行分析。
• Ensembl:/index.html 选择human 输入 ankh • 选择Gene,点击 GeneID ENSG00000154122 • 点击左边的Export data
寻找promoter区域
• 5 Flanking sequence 输入2000 • Options for FASTA sequence中Genomic选5 Flanking sequence, • deselect all • 点击Next(不管正反此法都适用)
如何查找基因的启动子及预测转录因子?

如何查找基因的启动子及预测转录因子?最近长链非编码RNA(lncRNA)很火热,好不容易找到了一个心仪的lncRNA(关于怎么找,我们之前也聊过:自己做测序、芯片;从别人的数据里挖据;或移植研究从其他疾病里扯一个过来验证),那么问题来了:分子有了,机制部分我该往哪个方向扯呢?很多人可能都会仔细寻找下游靶分子,以证明该lncRNA参与了xx调控,具有某个功能,表明该lncRNA分子在疾病发生发展过程中起到了很重要的作用。
其实,我们还可以往上游做,以丰富机制研究的深度。
今天我们就聊一聊,预测一下参与调控lncRNA表达转录因子的方法。
今天我们通过2个方式进行预测:方法1、需要用到UCSC、PROMO数据库首先,我们需要找到lncRNA的启动子序列。
打开UCSC数据库:举例:HOTAIR输入:HOTAIR点击GO点击红色的那个序列得到这么一个图,点击红色框,继续点击,得到这个界面,我们需要修改一些参数:转录起始位点上游2000nt和下游100nt区域为我们所选的启动子区。
SubmitOK,启动子序列有了。
拷贝下来。
接下来,我们打开PROMO数据库:在SelectSpecies进行部分设置,Submit另外,如果对转录因子有选择的话,也可以在SelectFactors中进行设置。
最后,我们点击SearchSites将刚刚得到的启动子序列粘贴进行。
另外,默认容错率15%,如果得到的转录因子过多,我们可以进行调整,设置成5%或0%。
Submit/cgi-bin/promo_v3/promo/promo.cgi?dirDB=TF_8.3&idCon=148645 228400&getFile=resumSearchRes.html我最终设置了容错率为15,一共得到了80个预测的转录因子。
那么这些转录因子都有可能与HOTAIR的表达相关,可能存在正向或负向的调控关系。
<可结合另两篇博文找相关系数:1.Oncomine: 一个肿瘤相关基因研究的数据库;2.CRN:肿瘤表型转录组数据库 >方法2、直接通过GeneCards数据库查找相关基因的转录因子选择第一个HOTAIR,得到这个界面,往下拉:点击:See All at QIAGEN得到了很多很多的预测转录因子。
查询启动子区及甲基化位点预测 20130914

如何查询基因的启动子区及甲基化位点的预测
案例:NR_028414
打开ncbi,选择”Gene”,输入“NR_028414 ”
查看“Genomic Context”
注意这个基因的位置范围(即45430060..45434643)
在染色体上的方向为正向(从左到右),即位置45430060之前为启动子区域
选择基因示意图
1)向下查看“Genomic regions, transcripts, and products”
2)将鼠标放在Genes的“NR_028412.1”示意图上
3)在弹出的窗口中点击
点击FASTA View
FASTA View的“45430060..45434643”代表的是NR_028412位置
出现该基因的实际序列
45430060代表起始位置
调整显示的位置
按刚才的基因范围调整一下这个数字:
一般起始位置(即45430060)向前推1000BP,向后推1000bp
更改基因范围后得到的序列,可以直接用于甲基化预测
将上面得到的序列,拷贝至以下网站:/cgi-
bin/methprimer/methprimer.cgi
点击submit,进入
结果显示有1000-1500区域段是可能发生甲基化的,后面那个蓝色区域距离有点远,因为这个基因的一号外显子本身是很短的,所以最终选择的片段如下:。
如何查找一个基因的启动子序列

如何查找一个基因的启动子序列关键词:基因启动子序列软件定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
这项搜寻要从UCSC基因组浏览器开始,网址为/。
以编码pendrin (PDS)的基因为例来说明上述问题。
PDS与耳蜗的异常发育、感觉神经性听力下降以及弥散性甲状腺增大(甲状腺肿)有关。
进入UCSC的主页后,在Organism的下拉菜单中选择Human,然后点击Browser。
使用者现在到了人类基因组浏览器入口。
本例的搜寻很简单:在assembly的下拉菜单中选择Dec. 2001,在position框中键入pendrin,然后点击Submit。
返回的页面结果显示一个已知的基因和两个mRNA序列。
继续点击mRNA序列的登录号AF030880,出现包含这个mRNA区域的图解概要。
为了获得这个区域更清晰的图像,点击紧靠zoom out的1.5X按钮。
最后点击页面中部的reset all按钮,使各个路径的设置恢复默认状态。
然而,对于本例的搜寻目的来说,默认设置不是理想的设置。
按照视图利用页面底部的Track Controls按纽,将一些路径设置为hide模式(即不显示),其他设置为dense模式(所有资料密集在一条直线上);另一些路径设置为full 模式(每个特征有一个分开的线条,最多达300)。
在考虑这些路径内究竟存在那些资料之前,对这些路径的内容和表现做一个简要的讨论是必要的,许多这些讨论是由外界提供给UCSC的。
下面是对基因预测方法的更进一步讨论,这些信息也可以在其他地方找到。
对于Known Genes(已知基因)和预测的基因路径来说,一般的惯例是以一个高的垂直线或块状表示每个编码外显子,以短的垂直线或块状表示5′端和3′端非翻译区。
寻找启动子区域和预测转录因子结合位点

寻找promoter区域
• 选择Promoter/Upstream by 2023 bases • Exons in upper case, everything else in lower case外显子大写,其他小写
寻找promoter区域
• 选择Promoter/Upstream by 2023 bases • Exons in upper case, everything else in lower case外显子大写,其他小写
寻找promoter区域
• 点击search product, 选择promoter clones,因为没有ANKH旳信息, 此处输入FIBRONECTIN
• 选择目旳基因
寻找promoter区域
• 点击click here to view the promoter sequence • 得到promoter信息
预测Transcription factor binding site
Step1 selectspecies选择human Step1 SelectFactors选择NF-kappaB [T00590] Step2 SearchSites输入ANKH旳promoter区域 成果中有一种位点TGGGAAATACCT,与JASPAR成果中得分最高旳相同
• 在前两张幻灯片中选择FASTA • 在右边Change region shown输入14871887到14873887 • Display options选择Show reverse complement • 能够直接得到FASTA格式旳promoter核苷酸序列(似乎有一种bp旳差距,能
够输入14871887到14873886 )
形
显示旳核苷 酸序列
你想做的chip启动子是怎么找到的?

你想做的chip启动子是怎么找到的?作者:凌风(转载请注:解螺旋·医生科研助手)你知道启动子在哪里么?LncRNA的研究炙手可热哇,表观遗传学机制方面你不得懂一点?不管是高大上的chip还是荧光素酶报告基因,都少不了启动子的序列,那么问题来了,启动子区的序列你会查么?图文解析来啦,这是小编最常用的方法啦,接地气,用神器----ucsc!1.打开ucsc,小编一般都用hg19版本,在下图中搜索明星分子BCL-2(why?因为它出名哇!!)。
2. 接下来你就看到这一堆堆线条,不对啊,bcl-2这个基因怎么显示的这么勉强,那就zoom out吧!zoom out 是缩小,这怎么记住呢?你想啊,你站的远看到的就多啦,是不是就能看到它的全貌了?是不是就把眼前的缩小了呢?3.站得远,看的清了,你就可以看到这个基因的全貌了,一般我们认为启动子很有可能是在TSS前2kb,或者TSS后1kb位置,所以我们就先看一下基因的转录方向,从起始不为前后各拉一段(敲黑板,划重点!)。
拉多长,你可看到那个标尺?根据标尺大小适当的拉~诺,就是像这样,大致拖个范围出来,就会弹出下面的框框,点zoom in 放大。
5.大致看一下,这个范围拉的还算合理,那我们就要取序列了,点“view”,再点“dna”,翻页再点“getDNA”就可以得到了!6.有了序列,再把外显子部分序列标注出来,你就可以随心所欲的来挑选设计启动子区引物了~如果你不会查外显子序列,那你就再往下看看:你不是搜索了BCL-2了么,在第2个图上面,你看到Refseq Gene了么?点它下面那条线,蓝色框框里面的:再点框框里的就看到它有几个外显子,序列是什么,中间隔着啥,都看到了:你懂了么?这个是小编最常用的,倾情奉献,当然也有很多其他方法,见仁见智啦!。
